Introducción
Staphylococcus aureus resistente a la meticilina (SARM) se disemina por todo el mundo, adaptándose a diferentes condiciones ambientales y modula su patogenicidad, debido a la capacidad de adquirir genes por transferencia horizontal o vertical (Schaberg y Zervos 1986), incluidos genes de resistencia a múltiples antibióticos. Desde los inicios de la era antimicrobiana se han seleccionado de manera gradual cepas de S. aureus resistentes a antibióticos de importancia para el uso clínico. SARM es uno de los principales patógenos infecciosos recientes y, por lo tanto, plantea un desafío para el control de infecciones (Liu et al. 2016). En 1959 surgió la meticilina; resistente a la penicilinasa que produce S. aureus. Dicho antibiótico pertenece al grupo de los β-lactámicos. Posee tamaño molecular mayor al de la penicilina (Aguayo-Reyes et al. 2018). La Organización Mundial de la Salud (OMS) ha clasificado a Staphylococcus aureus resistente a la meticilina (MRSA), con sensibilidad intermedia y resistencia a la vancomicina (VISA y VRSA), como un patógeno prioritario de Prioridad 2: Elevada para la investigación y desarrollo de nuevos antibióticos (OMS 2024). Actualmente, se han aislado SARM de alimentos de origen animal en diferentes países; sin embargo, sólo unos pocos estudios monitorean SARM en los alimentos, principalmente en los productos lácteos (González et al. 2017).
La intoxicación alimentaria estafilocócica (IAE) es una de las enfermedades más comunes transmitidas por alimentos en todo el mundo como resultado del consumo de alimentos que contienen enterotoxinas estafilocócicas (ES) producidos principalmente por S. aureus (Queiroga et al. 2013). Se conocen cinco tipos de enterotoxinas (A, B, C, D y E), de las cuales A es la más prevalente en los brotes de IAE (Hennekinne et al. 2012).
La leche y los productos lácteos se relacionan directamente con la frecuencia de aparición en la intoxicación alimentaria por estafilococos (Torres et al. 2021), y es mayormente asociado con brotes de intoxicación alimentaria (Kümmel et al. 2016, Aragão et al. 2021). La presencia de los microorganismos en el queso depende fundamentalmente de la calidad y tratamiento térmico de la leche, limpieza en general de la quesería, calidad de los cultivos empleados, manejo de la cuajada durante el procesamiento, temperatura de almacenamiento, transporte y distribución del queso (González-Machado et al. 2024). La comercialización de productos lácteos elaborados a partir de leche cruda, son una realidad en Latinoamérica, sobre todo en México, tanto en las comunidades rurales como en las áreas periurbanas de las ciudades (Adame-Gómez et al. 2018). Lo que aumenta el riesgo de consumir alimentos contaminados. Por ello el objetivo del artículo fue caracterizar molecularmente a Staphylococcus aureus resistente a meticilina (SARM) en quesos frescos artesanales expendidos en el mercado de Puerto Escondido, Oaxaca.
Materiales y métodos
Área de estudio
Los quesos frescos artesanales utilizados se adquirieron en el mercado local ubicado en la ciudad de Puerto Escondido, municipio de San Pedro Mixtepec, en el estado de Oaxaca, México.
Toma de muestras
Se efectuó un muestreo no probabilístico por conveniencia el día 24 de agosto de 2021 se realizó la compra de cuatro quesos de aro y cuatro de hoja (queso fresco envuelto en Xanthosoma robustum, Araceae) conocidos comúnmente como capote o colomo (Pacheco-Trejo et al. 2023), en tres queserías (A, B y C); mismas que aceptaron ser parte de dicho muestreo. Los quesos se etiquetaron y se transportaron en una bolsa de primer uso proporcionadas al vendedor y colocados en hielera para mantener una temperatura de aproximadamente 10°C y llevarlos para su posterior análisis a los laboratorios de Genética y Productos Pecuarios de la Universidad del Mar y al Instituto Nacional de Investigaciones Agrícolas y Pecuarias de la ciudad de Guadalajara.
Obtención de muestras compuestas
Con la finalidad de poder realizar los análisis fisicoquímicos y microbiológicos correspondientes, fue necesario obtener muestras compuestas con cantidades superiores a 700 g, para ello se realizó un muestreo aleatorio simple: técnica de cuarteo, en cada uno de los quesos adquiridos (4 quesos aro y 4 quesos hoja por quesería), y posteriormente se agruparon por tipo de queso y quesería de origen; denominadas con la literal de cada quesería (A, B y C) más la designada para el queso de aro (A) y el de hoja (H), de tal forma que se obtuvieron seis grupos nombrados: AA, AH, BA, BH, CA y CH. Al finalizar se empacaron al vacío 500 g de cada muestra, los cuales fueron identificados con sus respectivas claves y enviados al laboratorio de Nutrición Animal del Centro Universitario del Sur para que se realizaran por duplicado los análisis de humedad, proteína cruda, grasa cruda y cenizas; quienes, en vinculación con el Instituto Nacional de Investigaciones Agrícolas y Pecuarias de la ciudad de Guadalajara, determinaron dos veces los valores de cloruro de sodio, calcio y conductividad eléctrica. El material restante se colocó en bolsas de plástico y se guardó en un congelador para su posterior análisis. Todos los análisis se hicieron por duplicado.
Análisis fisicoquímicos
Temperatura y pH
Para la determinación de estas variables se utilizó un potenciómetro/termómetro con electrodo de inserción Hanna® modelo HI 99161.
Determinación de Lugol
Se tomaron 5 g de cada una de las muestras compuestas de queso y posteriormente se depositaron en un matraz Erlenmeyer de 250 mL, que contenía 100 mL de agua destilada, a continuación, se colocó el matraz sobre la parrilla eléctrica de calentamiento y agitación; THERMO SCIENTIFIC; modelo SP88850100. Al llegar al punto de ebullición, se procedió a dejarlo enfriar, para añadir unas gotas de Lugol (yodo y yoduro 1:2). Una coloración azul oscura; habría indicado la presencia de almidón, mientras que la tonalidad marrón indica un resultado negativo, como lo señala la NMX-F-374-1983 (SE 2021).
Calcio, cloruro de sodio y conductividad eléctrica
Cada una de las muestras compuestas se enviaron al Instituto Nacional de Investigaciones Agrícolas y Pecuarias en Guadalajara, Jalisco, donde se determinaron las variables Ca, NaCl mediante digestión con ácido nítrico y cuantificación mediante espectrofotómetro de absorción atómica, mientras que Conductividad eléctrica (CE) fue medida a través de un Conductímetro.
Análisis microbiológico
El análisis microbiológico se realizó en el laboratorio de Genética perteneciente a la Universidad del Mar Campus Puerto Escondido, donde se extrajo el ADN genómico de las muestras compuestas de los quesos y se realizó la amplificación por PCR multiplex utilizando primers para identificación y caracterización, virulencia y determinar el tipo de cassette cromosómico estafilocócico de resistencia a meticilina (SCCmec).
Cepa control
La cepa de referencia utilizada es Staphylococcus aureus subsp. Aureus (ATCC®43300™) proporcionada por el M.C. Carlos Alberto Castañón Sánchez del Hospital Regional de Alta Especialidad de Oaxaca. Una de las características importantes de S. aureus es su capacidad para secretar toxinas que dañan las membranas de las células del hospedero (Castañón-Sánchez 2012) cuyas características mecA positivo; SCCmec type II positivo; resistente a meticilina y oxacilina.
Extracción de ADN genómico
Las muestras de queso fueron desmoronadas con ayuda de guantes, se colocaron 2 g de muestra en un tubo Falcón de 50 mL estéril y se agregaron 10 mL de TEN (Tris-HCl 100 mmol, EDTA 50 mmol, NaCl 500 mmol a pH 8.0) y 5 perlas de vidrio para posteriormente ser agitadas en un vortex; DRAGONLAB MXS®, modelo 821200040000, durante 5 min, posteriormente se añadieron 20 mL de buffer lisis (Tris-HCl 100 mM pH 8.0, EDTA 20 mM pH 8:0, NaCl 1.4 M, CTAB 2%) (relación 1:2) se agitaron durante 5 min, se agregaron 120 µL de proteinasa k y 120 µL de lisozima se invirtieron los tubos lentamente, con el objetivo de mezclar las muestras, durante 10 min. Posteriormente, se transfirió 1 mL de las muestras a tubos eppendorf estériles y se incubaron a 67°C durante 30 min, en una parrilla de calentamiento y agitación de la marca THERMO SCIENTIFIC; modelo SP88850100. Se agitaron los tubos cada 5 min para homogeneizar las muestras, al terminar se centrifugaron a 12 000 rpm por 15 min. Después se procedió con la técnica de extracción fenol-cloroformo-isoamílico (Green y Sambrook 2012). Se verificó la extracción mediante electroforesis en gel de agarosa Promega, grado analítico al 0.8% (w/v) con buffer TAE 1X de la marca THERMO SCIENTIFIC®, como disolución de corrida. Se cargaron 5 µL del producto amplificado y 5 µL de buffer de carga a 60 volts por 37 min, utilizando para el proceso un equipo de electroforesis marca Bio-Rad®, modelo PowerPac™HC. Finalmente se tiñeron en bromuro de etidio (0.5 µg/mL) por 25 min, se observaron y fotografiaron en el transiluminador; UVP Benchtop® Variable Transilluminator.
Caracterización de Staphylococcus aureus
La caracterización de Staphylococcus aureus se realizó por PCR multiplex; para ello se usaron primers específicos descritos en la Tabla 1.
Tabla 1 Primers para identificación y caracterización de Staphylococcus aureus
| Gen | Nombre del Primer | Secuencia del primer | Tamaño (pb) | Referencia |
|---|---|---|---|---|
| 23S rRNA | StaphyF | ACGGAGTTACAAAGGACGAC | 1251 | El-Sayed et al. (2006) |
| StaphyR | AGCTCAGCCTTAACGAGTAC | |||
| Gen factor de adhesión | clfAF | GGCTTCAGTGCTTGTAGG | 900-1000 | El-Sayed et al. (2006) |
| clfAR | TTTTCAGGGTCAATATAAGC | |||
| Coagulasa (evasión inmunológica) | CoaF | ATAGAGATGCTGGTACAGG | 580-660 | Hookey et al. (1998) |
| CoaR | GCTTCCGATTGTTCGATGC | |||
| Termonucleasa (invasión) | nucF | AGTTCAGCAAATGCATCACA | 400 | Cremonesi et al.(2005) |
| nucR | TAGCCAAGCCTTGACGAACT |
Para la amplificación se usó un termociclador BioRad®, la mezcla de reacción (50 µL) que contenía 1X de buffer (Promega®), 0.5 mmol de MgCl (BioTecMol), 1.25 u/µL TaQ polimerasa (Promega®), 0.2 mmol dNTP´s (Sigma), primers 0.1 µM. Para el PCR multiplex de identificación y caracterización de Staphylococcus aureus las muestras se sometieron a ciclos térmicos donde la temperatura de alineación era de 94 °C durante 5 min, seguido de 30 ciclos, manteniendo desnaturalización a la misma temperatura por 1 min. Posteriormente hibridación a 64 °C por 2 min, 58 °C por 2 min y 57 °C por 2 min. Aunado a una extensión a 72° C por 90 seg y elongación final de 72 °C por 10 min; finalmente enfriar a -4° C. Posteriormente, se tomaron 5 µL de cada muestra resultante de la amplificación y se repitió el proceso con las mismas condiciones. Los productos de amplificación se analizaron por electroforesis en gel de agarosa grado analítico 2%, con buffer TAE 1X (40 mmol Tris-HCI, 1 mmol EDTA/l, 1.14 µL/L de ácido acético glacial, pH 7.8), se cargaron 25 µL del producto amplificado y 5 µL de buffer de carga a 80 volts por 2 horas, finalmente se tiño en bromuro de etidio durante 25 min y se observó el gel en el transiluminador.
Perfil de virulencia de aislamientos de Staphylococcus aureus
Para el perfil de virulencia de S. aureus se usaron primers los descritos en la Tabla 2.
Tabla 2 Primers para el Perfil de virulencia
| Proteína | Nombre del primer | Secuencia del primer | Tamaño (pb) | Referencia |
|---|---|---|---|---|
| Enterotoxina A | seaF | GGTTATCAATGTGCGGGTGG | 102 | Mehrotra et al. (2000) |
| seaR | CGGCACTTTTTTCTCTTCGG | |||
| Enterotoxina B | sebF | GTATGGTGGTGTAACTGAGC | 164 | Mehrotra et al. (2000) |
| sebR | CCAAATAGTGACGAGTTAGG | |||
| Enterotoxina C | secF | AGATGAAGTAGTTGATGTGTATGG | 451 | Mehrotra et al. (2000) |
| secR | CACACTTTTAGAATCAACCG | |||
| Enterotoxina D | sedF | CCAATAATAGGAGAAAATAAAAG | 278 | Mehrotra et al. (2000) |
| sedR | ATTGGTATTTTTTTTCGTTC | |||
| Enterotoxina E | seeF | AGGTTTTTTCACAGGTCATCC | 209 | Mehrotra et al. (2000) |
| seeR | CTTTTTTTTCTTCGGTCAATC | |||
| Toxina etA | etaF | GCAGGTGTTGATTTAGCATT | 93 | Mehrotra et al. (2000) |
| etaR | AGATGTCCCTATTTTTGCTG | |||
| Toxina etB | etbF | ACAAGCAAAAGAATACAGCG | 226 | Mehrotra et al. (2000) |
| etbR | GTTTTTGGCTGCTTCTCTTG | |||
| Toxina-1 del síndrome de choque tóxico | TSST-1 | ATGGCTATATACATTCAATT | 350 | Mullarky et al. (2001) |
| TSST-2 | TTTCCAATAACCACCCGTTT |
Para la amplificación se empleó un termociclador BioRad®, la mezcla de reacción (50 µL) que contiene 1X de buffer, 0.5 mmol de MgCl, 1.25 u/µL TaQ polimerasa (Promega®), 0.2 mmol dNTP´s (Sigma®), primers 0.08 µM. Las muestras fueron sometidas a ciclos térmicos donde la temperatura de alineación era de 94 °C durante 5 min, seguido de 30 ciclos adicionales, manteniendo desnaturalización a la misma temperatura por 2 min. Posteriormente, se realizó hibridación a 55°C por 2 min. Además de una extensión a 72 °C por 1 min y una elongación final de 72°C por 5 min. Conservación a -4°C. Posteriormente se tomaron 5 µL de cada muestra resultante de la amplificación y se repitió el proceso con las mismas condiciones. Los productos de amplificación se comprobaron por electroforesis en gel de agarosa al 2% con buffer TAE 1X (40 mmol Tris-HCI, 1 mmol EDTA/L, 1.14 µL/L de ácido acético glacial, pH 7.8), se cargaron 25 µL del producto amplificado y 5 µL de buffer de carga a 80 volts por 2 horas, se tiño el gel en bromuro de etidio y finalmente se observaron las bandas resultantes en el transiluminador.
Tipo de cassette cromosómico estafilocócico de resistencia a meticilina (SCCmec) en cepas de Staphylococcus aureus
Para la amplificación se utilizó un termociclador BioRad, la mezcla de reacción (50 µL) compuesto por 1X de buffer, 0.5 mmol de MgCl, 1.25 u/µL TaQ polimerasa (Promega), 0.2 mmol dNTP´s (Sigma), primers 0.08 µM. Las condiciones para la ampliación fueron 12 min para la elongación a 94°C, 30 ciclos de amplificación, 45 min para desnaturalización a 94 °C, 1 min para la hibridación a 55 °C y 1 min a 72 °C para el proceso de extensión se concluyó con una elongación final de 10 min a 72 °C y conservación a -4 °C. Los primers utilizados se describen en la Tabla 3.
Tabla 3 Primers para determinar el tipo de cassette cromosómico estafilocócico de resistencia a meticilina (SCCmec).
| SCCmec | Tipo | Nombre del Primer | Secuencia del primer | Tamaño (pb) | Referencia |
|---|---|---|---|---|---|
| Resistencia a meticilina | Control | mecAF | GAAATGGAACGTCCGATAA | 310 | Rahmaniar et al. (2020) |
| mecAR | CCAATTCCACATTGTTTCCTAA | ||||
| locus A | I | CIF F2 | TTCGAGTTGCTGATGAAGAAGG | 495 | Sánchez et al. (2013) |
| CIF R2 | ATTTACCACAAGGACTACCAGC | ||||
| locus B | II | KDP F1 | AATCATCTGCCATTGGTGATGC | 284 | Sánchez et al. (2013) |
| KDP R1 | CGAATGAAGTGAAAGAAAGTGG | ||||
| locus C | II, III | MECI P2 | ATCAAGACTTGCATTCAGGC | 209 | Sánchez et al. (2013) |
| MECI P3 | GCGGTTTCAATTCACTTGTC | ||||
| locus D | I, II, IV | DCS F2 | CATCCTATGATAGCTTGGTC | 342 | Sánchez et al. (2013) |
| DCS R1 | CTAAATCATAGCCATGACCG | ||||
| locus E | III | RIF4 F3 | GTGATTGTTCGAGATATGTGG | 243 | Sánchez et al. (2013) |
| RIF4 R9 | CGCTTTATCTGTATCTATCGC | ||||
| locus F | III | RIF5 F10 | TTCTTAAGTACACGCTGAATCG | 414 | Sánchez et al. (2013) |
| RIF5 R13 | GTCACAGTAATTCCATCAATGC | ||||
| locus G | IA | IS431 P4 | CAGGTCTCTTCAGATCTACG | 381 | Olivera (2002) |
| pUB110R1 | GAGCCATAAACACCAATAGCC | ||||
| locus H | IIIA | IS431 P4 | CAGGTCTCTTCAGATCTACG | 303 | |
| pT181 R1 | GAAGAATGGGGAAAGCTTCAC |
Resultados
Análisis fisicoquímicos
La prueba de Lugol que se realizó para determinar la presencia de almidón se traduce en un indicativo de si el producto es análogo o de leche. Los quesos de las tres queserías resultaron negativos para la prueba, por lo que se determina que son de leche. En el caso de los quesos frescos artesanales el valor mínimo registrado para la variable calcio fue de 15.14 ± 0.27 resultado de la muestra AH y como máximo 28.94 ± 0.66 obtenido de quesería CH (Tabla 4). Los quesos frescos artesanales adquiridos en el mercado de Puerto Escondido tienen altos contenidos de calcio. Para los niveles de NaCl, los valores encontrados para este compuesto van desde 4.2% que pertenece a la muestra de la quesería AH, hasta 6.5% encontrado en la quesería CH. Aun cuando los quesos del presente estudio cuentan con altos contenidos de NaCl, S. aureus. Con relación a la conductividad eléctrica es una medida indirecta de la concentración de sales de una solución y de su contenido bacteriano, la causa radica en que las sales son buenas conductoras de electricidad y las bacterias generan electricidad cuando respiran, el rango encontrado varió entre 1.32 ± 0.02 dS/m, correspondiente a la quesería AH, y 1.87 ± 0.02 dS/m, representando a la quesería B.
Tabla 4 Comparación entre parámetros de crecimiento de S. aureus y resultados fisicoquímicos.
| Parámetros de crecimiento de S. aureus. | Muestras | |||||||
|---|---|---|---|---|---|---|---|---|
| Parámetros | Crecimiento de S. aureus | Producción de enterotoxinas | AA | AH | BA | BH | CA | CH |
| Rango | ||||||||
| Temperatura (°C) | 7-48 | 10-48 | 26.36 | 24.11 | 25.06 | 25.67 | 24.86 | 25.00 |
| pH | 4-10 | 4.0-9.6 | 6.01 | 6.12 | 6.27 | 6.22 | 6.20 | 6.44 |
| aw | 0.83- > 0,99 0-90- > 0,99 | 0.85 - > 0,99 | ND | ND | ND | ND | ND | ND |
| 0.90 - > 0,99 | ||||||||
| NaCl (%) | 0-20 | 0-10 | 5.77 | 4.19 | 4.25 | 4.84 | 4.61 | 6.45 |
| Calcio (g/kg) | ND | ND | 20.50 ± 7.05 | 15.14 ± 0.27 | 15.57 ± 0.42 | 16.30 ± 0.70 | 27.99 ± 5.38 | 28.94 ± 0.66 |
| Conductividad eléctrica (dS/m) | ND | ND | 1.48 ± 0.22 | 1.32 ± 0.02 | 1.58 ± 0.01 | 1.87 ± 0.02 | 1.54 ± 0.04 | 1.63 ± 0.02 |
| Atmósfera | Aerobia-anaerobia | Aerobia-Anaerobia | Ae | Ae | Ae | Ae | Ae | Ae |
aw = Actividad de agua, NaCl = Cloruro de sodio, Ae = Aerobia, ND = No determinado.
Caracterización de Staphylococcus aureus.
Se amplificaron los genes 23S rrna (1251 pb) y coa (660 pb) en todas las muestras (Figura 1). Sin embargo, no se logró la amplificación de los genes del factor de adhesión (clfa) y termonucleasa (nuc), probablemente debido a la variabilidad genética ya que algunos genes pueden estar ausentes o presentar mutaciones que impiden su amplificación.
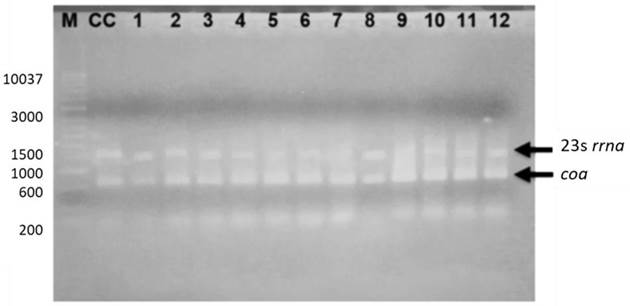
Figura 1 Productos de PCR multiplex para la identificación de S. aureus en quesos frescos artesanales expendidos en el mercado de Puerto Escondido, mediante gel de agarosa al 2%. Carriles: M. Marcador Hyperladder 1Kb, CC. Cepa Control (ATCC 43300), 1. AA, 2. AA, 3. AH, 4. AH, 5. BA, 6. BA, 7. BH, 8. BH, 9. CA, 10. CA, 11. CH y 12. CH.
Perfil de virulencia de aislamientos de Staphylococcus aureus
Los genes que amplificaron (Figura 2) fueron el gen tsst (350 pb) que codifica para la toxina TSST-1 en todas las muestras que pertenecen a la quesería A (carril 1 y 2) y sólo 1 perteneciente a la quesería C (carril 9), el gen see (209 pb) que codifica para la enterotoxina E fue detectada en todas las muestras de las tres queserías.
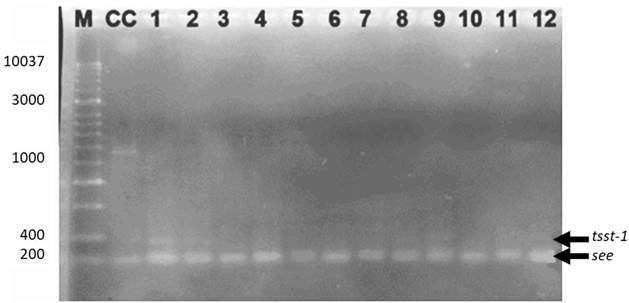
Figura 2 Producto de PCR multiplex para la determinación del perfil de virulencia. En quesos frescos artesanales expendidos en el mercado de Puerto Escondido, mediante gel de agarosa al 2%. Carriles: M. Marcador Hyperladder 1Kb, CC. Cepa Control (ATCC 43300), 1. AA, 2. AA, 3. AH, 4. AH, 5. BA, 6. BA, 7. BH, 8. BH, 9. CA, 10. CA, 11. CH y 12. CH.
Tipo de cassette cromosómico estafilocócico en cepas de Staphylococcus aureus
Se detectó una banda que corresponde al locus D (342 pb), tal y como se observa en la Figura 3. Dicho resultado es análogo para todas las muestras evaluadas. El locus D es un indicativo de la presencia de los SCCmec I, II y IV. Sin embargo, para que el cassette I se considere positivo, debe también amplificarse el locus A, mientras que los locus B y C confirmarían la presencia del SCCmec II. A partir de lo anterior, al no haber amplificación del locus A, B y C.
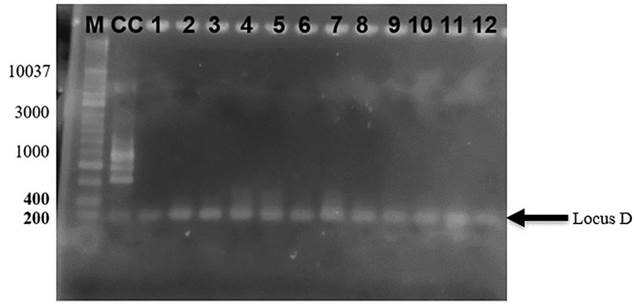
Figura 3 Producto de PCR multiplex para la detección del tipo de SCCmec. En quesos frescos artesanales expendidos en el mercado de Puerto Escondido, mediante gel de agarosa al 2%. Carriles: M. Marcador Hyperladder 1Kb, CC. Cepa Control (ATCC 43300), 1. AA, 2. AA, 3. AH, 4. AH, 5. BA, 6. BA, 7. BH, 8. BH, 9. CA, 10. CA, 11. CH y 12. CH.
Discusión
Análisis fisicoquímicos.
Aunque Staphylococcus no utiliza la respiración extracelular (Pasachova-Garzón et al. 2019), su actividad metabólica puede influir en la composición iónica del queso. Por ejemplo, la fermentación llevada a cabo por estas bacterias puede producir ácidos y otros compuestos que afectan la concentración de iones en el queso, alterando su conductividad eléctrica. La actividad del agua (aw) es una propiedad termodinámica principal en ciencia y tecnología de alimentos, el uso de la sal (NaCl) y otros componentes como el calcio (Ca2+) se utilizan para reducir la actividad del agua en el queso, limitando el crecimiento bacteriano que generalmente oscila entre 0.95 y 0.991 (Tapia 2020). Pero este rango permite el crecimiento de Staphylococcus aureus y la producción de las toxinas, 4.19 a 6.45% de NaCl de los quesos muestreados (Alejo et al. 2011). Los quesos analizados presentaron alto porcentaje de NaCl, superando lo reportado por Van-Hekken y Farkye (2003) donde el contenido de NaCl fue de 1 a 3% en quesos frescos.
El calcio fue de 15.14±0.27 como mínimo hasta 28.94±0.66 como máximo, por lo que de acuerdo con Domínguez et al. (2004), el calcio (Ca²⁺) desempeña un papel vital en muchos procesos bacterianos, incluyendo la expresión genética y la virulencia. Al respecto King et al. (2020) reportan que el calcio regula la virulencia bacteriana actuando como un señalizador celular, permitiendo la comunicación y respuesta celular tanto en ambientes intracelulares como extracelulares. Además, mencionan como los patógenos bacterianos reconocen y responden al calcio del huésped, lo que desencadena mecanismos moleculares de adhesión, formación de biopelículas, daño celular del huésped y resistencia a las defensas del huésped. El calcio también regula eventos clave en la colonización del huésped y la virulencia bacteriana, facilitando el desarrollo de infecciones persistentes. Al comparar estas variables con las condiciones de crecimiento de la bacteria (Tabla 4), se observa que los quesos artesanales comprados en queserías del mercado de Puerto Escondido, Oaxaca son microambientes idóneos para el crecimiento y la producción de toxinas de S. aureus (Alejo et al. 2011).
Caracterización de Staphylococcus aureus
El 100% de las 6 muestras compuestas (24 quesos) presentaron presencia de S aureus coagulasa positiva, lo cual es comparable con lo reportado en otras regiones de México. Por ejemplo, en el municipio de Teotitlán de Flores Magón, en el estado de Oaxaca en México, González-Montiel y Franco-Fernández (2015), establecieron la composición de la microbiota del queso de aro que ahí se comercializa. Para ello analizaron 12 muestras de queso, la cantidad de S. aureus obtenidas por método tradicional fue de 5.76 ± 0.71 Log10 UFC/g, y en placa Petri fue de 5.98 ± 0.65 Log10 UFC/g., Por otro lado, en Chilpancingo Guerrero, México, Adame-Gómez et al. (2018) reportaron que, el 56.4% de 78 quesos elaborados con leche de vaca no pasteurizada fueron positivos para S. aureus. Para el Golfo de México, Guzmán-Hernández et al. (2016) reportan que el 36% de las muestras analizadas contenían S. aureus. Por otro lado, se ha encontrado la presencia de esta bacteria en quesos frescos en Colombia (Vanegas et al. 2008, Herrera y Santos 2015); Ecuador (Saltos et al. 2018); Venezuela (Maldonado y Llanca 2008); Brasil (Komatsu et al. 2010 ) e Irán (Shanehbandi et al. 2014). Resaltando la presencia de esta bacteria en los quesos frescos artesanales
Perfil de virulencia de aislamientos de Staphylococcus aureus
El gen que codifica para la enterotoxina E (see) se identificó en el 100% muestras de queso, encontraste, Shanehbandi et al. (2014) hallaron que 34.8% de sus aislados provenientes de queso fresco, eran positivos para sea, 13% seb, 4.3% sec y 8.7% see. La enterotoxina estafilocócica E es un superantígeno que, como tal, posee características inmunomoduladoras, es termoestable, producida durante la fase logarítmica del crecimiento bacteriano y es resistente a los jugos gástricos que se encuentran en el estómago de los hospedadores. Además de ser responsable de intoxicaciones alimentarias que presentan síntomas como diarrea y vómito, e incluso puede generar cuadros de enterocolitis. El principal medio de transferencia hacia los quesos de cepas enterotoxigénicas es por contaminación cruzada, mediante el personal que los elabora y manipula, seguido de animales que padecen mastitis clínica o subclínica (Alejo et al. 2011, Cervantes-García et al. 2014).
En cuanto a la toxina responsable del síndrome del choque tóxico (TSST-1), sólo en tres muestras de queso se detectó el gen tsst (25%), mientras que Ghasemi y Mahdavi (2018) determinaron que 2 de 22 aislamientos de S. aureus provenientes de quesos locales en el noreste de Irán, contenían el gen tsst-1. Mientras que Arcuri et al. (2010) al analizar 166 aislados de S. aureus de leche cruda de vaca contenida en tanques de enfriamiento de Minas en Brasil, identificaron el gen tsst-1 en 8 aislamientos. Al respecto, tsst-1 es uno de los agentes involucrados en causar la mastitis clínica y subclínica en animales domésticos como vacas, ovejas y cabras por lo que su presencia puede considerarse proveniente de una ruta de transmisión de la leche hacia los alimentos que de ella se generan (Zschöck et al. 2000, Farahmand et al. 2013).
Tipo de cassette cromosómico estafilocócico en cepas de Staphylococcus aureus
Se detectó el locus D tipo IV en todas las muestras compuestas de queso, caso similar fue reportado por Herrera et al. (2016) quienes por tipificación genética de 8 aislamientos de SARM de muestras de queso fresco (doble crema) producido con leche cruda de vaca en pequeñas lecherías, determinaron que todos los aislamientos albergaban el SCCmec tipo IV. Las distintas estructuras genéticas del complejo de genes mec y del complejo de genes ccr determinan los tipos y subtipos de SCCmec y, por otro lado, en las regiones J puede estar integrada información de resistencia a otros antibióticos y metales pesados (Liu et al. 2016). Los aislamientos del tipo IV provienen de personas no asociadas al ambiente hospitalario han demostrado una mayor agresividad, lo que agrava las infecciones causadas por SARM (Cavalcante et al. 2013). Aunque se creía que ciertos tipos de SCCmec solo podían identificarse en aislamientos hospitalarios o comunitarios, estas cepas se han aislado en ambos entornos. Esto facilita una diseminación eficiente, convirtiéndose en un problema de salud pública (Shankar et al. 2020).
Conclusiones
Los resultados indican que los quesos de queserías del mercado de Puerto Escondido, Oaxaca, son microambientes propicios para el crecimiento y la producción de toxinas de Staphylococcus aureus, lo que representa un riesgo para la salud pública local. Los datos obtenidos pueden servir como base para desarrollar estrategias de intervención que incluyan la capacitación de productores en buenas prácticas de higiene y la regulación sanitaria más estricta en los mercados locales. Este trabajo subraya la necesidad de educar a la población sobre los riesgos asociados al consumo de productos lácteos no pasteurizados y la importancia de adquirir alimentos de fuentes confiables. La colaboración entre autoridades sanitarias, productores y consumidores es esencial para mejorar la calidad y seguridad de los alimentos en la región.
















