Introducción
Norovirus (NoV) son una de las causas más comunes de gastroenteritis viral en humanos y animales (Chhabra et al., 2019). Son el agente etiológico más común de la gastroenteritis aguda (Ahmed et al., 2014) y son responsables de aproximadamente el 20 % de todos los casos de gastroenteritis aguda en todo el mundo, con una prevalencia similar en países de ingresos altos y bajos (Liao et al., 2021).
NoV, es miembro de la familia Caliciviridae, su genoma está compuesto por un ARN lineal de sentido positivo, que tiene aproximadamente 7,6 kb de longitud (Jiang et al., 1993). Posee tres marcos de lectura abiertos (ORF) 1, 2 y 3, que codifican seis proteínas virales (VP). ORF-2 y ORF-3 codifican los componentes estructurales del virión VP1 y VP2; ORF-1 codifica proteínas no estructurales, incluyendo la proteasa del NoV y la ARN polimerasa dependiente de ARN (Thorne y Goodfellow, 2014).
Actualmente se organiza en diez genogrupos (G) (GI a GX), que se dividen en 50 genotipos. Los genogrupos que se han identificado en humanos son GI, GII, GIV.1, GVIII y GIX, en animales se identifican una amplia variedad de genogrupos: porcinos (GII.11, GII.18 y GII.19), bovinos (GIII.1 y GIII.2), ovinos (GIII.3), roedores (GV.1 y GV.2), felinos (GIV.2, GVI.1 y GVI.2), leones (GIV.2), caninos (GVI.1, GVI.2 y GVII), marsopas comunes (GNA1), leones marinos (GNA2) y murciélagos (GX) (Villabruna et al., 2021).
Los antígenos del grupo histosanguíneo humano (HBGA) y, en particular, las familias fenotipos Lewis, Secretor y ABO, sirven como receptores de unión al NoV (Dabelsteen, 2002; Marionneau et al., 2001). Se ha demostrado que algunos animales expresan receptores de la familia HBGA, los cuales favorecen la infección por NoV, las especies reportadas son murinos (Taube et al., 2009), bovinos (Zakhour et al., 2009), caninos (Caddy et al., 2014), y murciélagos (Kocher et al., 2018). Los conejos también expresan receptores de unión HBGA (A, B y H tipo 2 [Lewis Y]) en la región del duodeno, además de otras regiones anatómicas, como tráquea y conductos biliares donde se expresan débilmente varios tipos de HBGA (Nyström et al., 2011). Los porcinos no expresan receptores HBGA, sin embargo, sí desarrollan infecciones por NoV aunque se desconocen los receptores (Silva et al., 2015).
El sector de cunicultura en México implementa la cría, engorda y reproducción de conejos con el objetivo de obtener carne blanca de alta calidad para el consumo humano, ya que esta carne tiene un porcentaje alto de proteínas, vitaminas y minerales, y además es reducida en calorías, grasas y colesterol (SADER, 2016). Las características que tiene la carne de conejo son aprovechadas para solucionar problemas de desnutrición que afectan a poblaciones vulnerables y/o de escasos recursos económicos en varios estados de la república mexicana (Jaramillo et al., 2015).
México tiene un inventario de 11 560 unidades de producción (UP) que reportan un inventario de 1 108 350 conejos domésticos. El Estado de México se mantiene desde el 2012 como principal líder productor y consumidor de carne de conejo a nivel nacional y posee un inventario de 66.806 vientres registrados en 3 885 UP y 293 332 conejos (SENASICA, 2020). Esta producción se encuentra relacionada principalmente con el corredor turístico “los Volcanes” y “la Ruta de Sor Juana”, que comprende los municipios de Tepetlixpa, Ozumba y Amecameca (EdoMex, 2017). En el país, la cunicultura se clasifica en tres tipos: tecnificada, semitecnificada y de traspatio, esta última se desarrolla comúnmente con escasas medidas sanitarias (SENASICA,2020b). Las razas que se emplean comúnmente para la producción de carne son las siguientes: Nueva Zelanda Blanco, California, Chinchilla, Mariposa, Satinado rojo, Azteca negro e híbridos (Comité Sistema Producto Cunícola, 2012).
Materiales y métodos
La presente investigación es cualitativa, en la que se realizó un estudio descriptivo, comparativo, observacional, de corte transversal, no experimental e intencional. Se empleó un muestreo no probabilístico y a conveniencia con la finalidad de manifestar que hay determinado rasgo en una población de estudio.
La población de estudio fue conformada por conejos con presencia de cuadros entéricos, de 35-65 días de edad, de todas las razas y de ambos sexos de UP cunícolas dentro de la región I del Estado de México, que comprende los municipios de Valle de Chalco, Chalco, Temamatla, Cocotitlán, Tlalmanalco, Juchitepec, Tenango del Aire, Ayapango, Amecameca, Atlautla, Ozumba, Tepetlixpa y Ecatzingo.
El periodo del estudio de campo se realizó de diciembre 2021 a diciembre 2022, donde también se recolectó información por medio de un cuestionario con datos de interés sobre las generalidades de las unidades de producción cunícolas.
Las muestras obtenidas para la realización de este estudio fueron heces de conejos de UP cunícolas, las cuales se recolectaron e identificaron en bolsas estériles para su fácil manejo, se trasportaron en termos refrigerados de 4-8 °C para su procesamiento, análisis y almacenamiento al Laboratorio de Biotecnología, Biología Molecular y Genética del C.U UAEM Amecameca.
Se realizó la extracción de ARN total de manera individual, utilizando la técnica descrita de fenol-cloroformo con Trizol de invitrogen®. El ARN extraído se almacenó en congelación a -75 °C hasta su análisis. Posteriormente se realizó la síntesis de ADNc con el kit comercial ImProm-II™, sistema de transcripción inversa siguiendo las instrucciones del fabricante.
Para la identificación molecular y amplificación de NoV, se empleó la Reacción en Cadena de la Polimerasa (PCR), utilizando los oligoiniciadores reportados por Kojima et al. (2002), dirigidos a la región de la cápside, los cuales son muy eficientes para la amplificación y el diagnóstico rápido de la infección por NoV, donde se obtiene un fragmento de 300 pares de bases (pb). La PCR fue realizada con las siguientes condiciones: desnaturalización inicial 94°C por 5 minutos 40 ciclos; desnaturalización 94°C por 30 segundos, alineamiento 50° C por 30 segundos y extensión de 72°C por 40 segundos, con una extensión final de 72°C de 5 minutos. Los productos de PCR se separaron en geles de agarosa al 3%, utilizando una electroforesis a 100 volts durante 30 minutos, posteriormente los geles se tiñeron con bromuro de etidio para ser visualizados en transiluminador UV.
Resultados
La población total fue de 5 327 conejos pertenecientes a 15 granjas productoras de carne de los municipios de la región I, del Estado de México. Dentro de esta población, se identificaron y obtuvieron muestras de 94 conejos con signología entérica, en las que, mediante el análisis molecular empleando los oligoiniciadores diseñados por Kojima et al. (2002), se identificó a NoV a través de RT-PCR un total de 21 muestras representando una frecuencia de 22.34% de NoV en conejos de las UP cunícola.
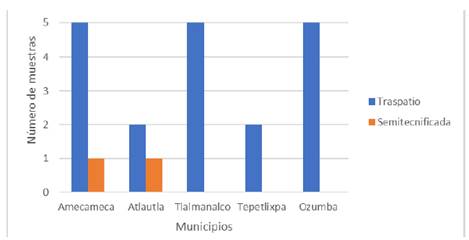
Los conejos positivos a NoV fueron recolectados en granjas pertenecientes a los municipios de Tlalmanalco, Amecameca, Atlautla, Ozumba y Tepetlixpa, como se observa en la tabla1.
Tabla 1 Procedencia de conejos positivos a NoV y tipo de producción.
| Municipio de procedencia | Tipo de producción | Identificación de conejo |
|---|---|---|
| Amecameca | Traspatio | C20 |
| Atlautla | Traspatio | C22 |
| Tlalmanalco | Semitecnificada | C24 |
| Tlalmanalco | Semitecnificada | C25 |
| Tepetlixpa | Traspatio | C27 |
| Tlalmanalco | Semitecnificada | C28 |
| Tlalmanalco | Semitecnificada | C29 |
| Tlalmanalco | Semitecnificada | C30 |
| Ozumba | Traspatio | C32 |
| Ozumba | Traspatio | C33 |
| Ozumba | Traspatio | C35 |
| Atlautla | Semitecnificada | C38 |
| Amecameca | Traspatio | C40 |
| Amecameca | Traspatio | C41 |
| Amecameca | Traspatio | C42 |
| Ozumba | Traspatio | C45 |
| Ozumba | Traspatio | C46 |
| Amecameca | Semitecnificada | C49 |
| Atlautla | Traspatio | C58 |
| Tepetlixpa | Traspatio | C62 |
| Amecameca | Traspatio | C69 |
Fuente. Elaboración propia.
Los resultados obtenidos indican que las muestras positivas a NoV se obtuvieron mayormente de UP de traspatio (90.48%) y en menor porcentaje de UP semitecnificada (9.52%), como se observa en la figura 1:
Fuente: Elaboración propia.
Figura 1 Tipo de producción asociado a conejos positivos a NoV pertenecientes a UP del Estado de Mexico.
La infección por NoV predominó en conejos híbridos obtenidos principalmente de la cruza de Nueva Zelanda y California 13/21 (61.91%) y de la raza California en 8/21 (38. 09%).
Discusión
Los NoVs son genéticamente diversos, infectan a una amplia gama de huéspedes mamíferos incluido el humano y son de distribución mundial (Kapikian et al., 1972). Las infecciones por NoV representan una carga económica mundial que haciende a los 60 mil millones de dólares (Bartsch et al., 2016).
Aunque todavía no se ha identificado un receptor celular definitivo para los NoVs, se ha demostrado que los receptores HBGA se unen a la proteína VP1 y facilitan la unión y/o entrada en la célula (Rockx et al., 2005). Tal como lo refieren Nyström et al. (2011), los conejos expresan receptores HBGA en células epiteliales intestinales haciéndolos susceptibles a la infección por NoV, y demostrado en este estudio mediante la implementación de los oligoiniciadores reportados por Kojima et al., (2002), los cuales permiten un diagnóstico de NoV rápido, específico y altamente sensible a través de la RT-PCR.
En este estudio, también se observó que los conejos que fueron positivos a la infección por NoV presentaron episodios diarreicos agudos, tal como se ha relacionado en brotes reportados de otras especies animales, como bovinos (Di Felice et al., 2016), porcinos (Shen et al., 2012), felinos (Pinto et al., 2012) y caninos (Mesquita y Nascimento, 2012). Sin embargo, no se descarta que los animales que no presentaron signología entérica no estén infectados con NoV, ya que un estudio epidemiológico realizado en ovinos asintomáticos reporta la detección de NoV (Wolf et al., 2009).
Las enfermedades que se presentan en las UP cunícola son un factor de gran importancia para la cunicultura, ya que disminuyen la rentabilidad y, por ende, la economía de los productores (Lebas et al., 2002).
El desarrollo de la cunicultura en México depende de factores agroecológicos, sociales, económicos y tecnológicos (Vélez et al., 2021); sin embargo, también es necesario incluir estudios que fortalezcan el factor zoosanitario epidemiológico en el que se realice la identificación de todos los patógenos que influyen en los procesos productivos y con ello contribuir al desarrollo de esta actividad.
Más del 90% de las muestras de heces de los conejos con signología entérica positivas a NoV son procedentes de granjas de traspatio, donde tal como lo reporta Reynoso et al. (2019), la producción es deficiente en infraestructura y manejo, además existe una estrecha relación con otras especies animales, como caninos, felinos, porcinos, equinos, ovinos y aves de engorda, lo cual puede favorecer a la transmisión interespecies de distintas enfermedades, así como la presentación de posibles eventos zoonóticos.
En México y en el mundo, el sector ganadero enfrenta crisis asociadas a la pandemia por COVID-19 (CEPAL, 2020). La cunicultura no fue la excepción, sino que además enfrentó un rebrote de Fiebre Viral Hemorrágica del conejo que afectó alrededor de dos mil 113 familias que viven de la cunicultura, principalmente en Estado de México, Aguascalientes, Hidalgo, Jalisco, Puebla y Tlaxcala (SENASICA, 2021), generando importantes pérdidas económicas estimadas en millones de pesos (Infobae, 2020).
Conclusiones
Se ha comprobado que, NoV también infectan a la especie (Oryctulagus cuniculus); generalmente las infecciones están asociadas a la presencia de diarreas en conejos de UP cunícola de traspatio.
La industria de la carne de conejo en México todavía está en la etapa de tránsito. Sin embargo, esta tiene un gran potencial de desarrollo ya que cumple con la demanda del consumidor en términos nutricionales y además apoya la economía nacional.
Contribuciones a futuras líneas de Investigación
Es necesario continuar monitoreando y/o vigilando las infecciones producidas por los NoVs en las UP cunícola, para lograr la secuenciación del genoma completo de NoV y, de esta manera, contribuir en la identificación de cepas que infectan a los conejos y su relación con los NoV que contagian a los humanos, a fin de aportar nueva información que ayude a dilucidar el posible potencial zoonótico de NoV.










 nova página do texto(beta)
nova página do texto(beta)