Introducción
La lechuga (Lactuca sativa), una especie anual autógama de clima frío, es una de las plantas más cultivadas del mundo. En mayo de 2024, se observaron plantas de lechuga variedad Iceberg cuyas hojas presentaron manchas necróticas de color bronceado a marrón oscuro, con deformaciones y atrofiamiento en su crecimiento (Figura 1), en un campo comercial ubicado en Guanajuato, México (DD: 21.242194, -100.881768). Además, se detectó una alta incidencia de trips (Frankliniella occidentalis) en la misma área, donde se tenían plantas de maíz en un campo adyacente y plantas de lechuga. Esta especie de trips es conocida por ser vector de múltiples virus fitopatógenos. Con base en esta información y a la literatura científica, el objetivo fue identificar la presencia de Orthotospovirus impatiensnecromaculae (Impatiens necrotic spot virus, INSV) en el cultivo de lechuga en Guanajuato, México.

Figura 1 Plantas de lechuga sintomáticas infectadas con Orthotospovirus impatiensnecromaculae observadas durante el estudio de campo.
Para la detección del INSV en muestras de campo, se recolectaron 12 plantas sintomáticas de manera aleatoria. Las muestras se analizaron con inmunotiras específicas para este virus (Agdia, EE. UU.). Esta técnica se basa en la inmunocromatografía de flujo lateral, utilizando anticuerpos específicos que producen líneas visibles (indicadores) al sumergirse en el extracto de muestra (savia). De acuerdo con este análisis 10 de las 12 muestras analizadas fueron positivas.
El material vegetal se envió y almacenó en el Centro de Bioingeniería del Tecnológico de Monterrey, campus Querétaro, donde se realizó el análisis molecular. Para confirmar la presencia de INSV, se extrajo ARN total de 12 muestras de tejido con el reactivo TRIzol siguiendo los lineamientos del fabricante (Meng y Feldman, 2010). Para la transcripción inversa-PCR (RT-PCR) de un solo paso, se utilizaron cebadores específicos (INSVF: 5′CCCAACTGCCTCTTTAGTGC3′ y INSVR: 5′GGACAATGGATCTGCTCTGA3′), siguiendo el protocolo previamente descrito por González-Pacheco y Silva-Rosales (2013), y que amplifica un fragmento genómico del segmento S. La transcriptasa inversa (RevertAid) y el ADN polimerasa (DreamTaq) fueron de ThermoFisher Scientific (EE. UU.). Como resultado, la reacción de RT-PCR generó el producto esperado (fragmento de 250 pb) en las mismas 10 muestras de lechuga detectadas previamente con inmunotiras. Los productos amplificados se enviaron a secuenciación Sanger en Macrogen Inc. (Corea), y las secuencias idénticas entre sí (GenBank: PQ151798) mostraron una identidad de 99 % con un aislado de INSV reportado en EE. UU. (GenBank: KX790323). Se realizó un análisis filogenético basado en la región secuenciada y las secuencias de aislados seleccionados de O. impatiensnecromaculae y O. tomatomaculae (tomato spotted wilt virus, TSWV) utilizando el software MEGA7 (Figura 2).
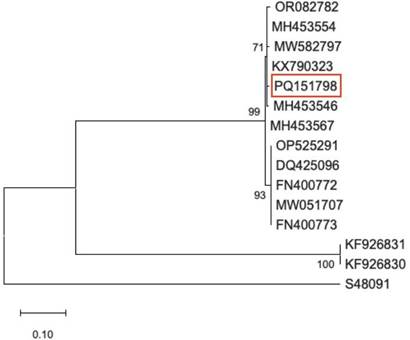
Figura 2 Árbol filogenético de máxima verosimilitud de múltiples aislados de Orthotospovirus impatiensnecromaculae (Impatiens necrotic spot virus, INSV) disponibles en GenBank. Secuencia generada durante este estudio es indicada con rojo. GenBank: S48091 corresponde a el Orthotospovirus tomatomaculae (tomato spotted wilt virus, TSWV) y es incluido en el análisis filogenético como grupo externo.
En México, O. impatiensnecromaculae está identificado en tomatillo (Physalis ixocarpa) y pimiento (Capsicum spp.) en Guanajuato y Querétaro (González-Pacheco y Silva-Rosales, 2013). Durante la preparación de este manuscrito, se reportó el virus en muestras de lechuga Iceberg recolectadas en el Estado de México y Puebla, las cuales mostraban síntomas de amarilleamiento, manchas necróticas marrones y anulares en las hojas y nervaduras centrales (Quevedo et al., 2024). Recientemente, se presentaron brotes graves de O. impatiensnecromaculae, con una incidencia hasta del 27 %, en campos comerciales de lechuga en California, EE. UU., y relacionados con altas poblaciones de
F. occidentalis, el vector natural del virus (Koike et al., 2008; Kuo et al., 2014). Dado que este insecto desempeña un papel crucial en la propagación del virus, es posible que, en Guanajuato, la proximidad de diversos cultivos facilita el movimiento de trips vectores entre campos, lo que provoca la infestación de cultivos más susceptibles, como la lechuga. Este es el primer reporte de INSV infectando plantas de lechuga en la región del Bajío, México. El Bajío es una de las zonas agrícolas más importantes de México e incluye estados de Guanajuato, Aguascalientes, Querétaro, Jalisco y Michoacán. Por lo tanto, se deben implementar prácticas de manejo efectivas, recalcar la importancia del estudio de vectores putativos para prevenir la propagación del O. impatiensnecromaculae a otros campos comerciales y evitar pérdidas económicas. En ese sentido, el desarrollo de cultivares resistentes a INSV y las estrategias de manejo integrado de plagas serán cruciales para abordar estos desafíos y garantizar la salud y la productividad a largo plazo
de los cultivos, incluyendo lechuga.










 texto em
texto em