
Adsorción de proteínas por afinidad en procesos por lotes: modelación, estimación de parámetros y simulación
Armando Tejeda-Mansir,1* Ivan Búsani,2 Ma. Eugenia Rentería2 y Rosa Ma. Montesinos2
1 Departamento de Investigaciones Científicas y Tecnológicas. Universidad de Sonora. Apartado Postal 593. Hermosillo 83000, Sonora, México. Tel: + 52(662) 212-1995; Fax: +52 (662) 2 12-3271. E-mail: atejeda@guayacan.uson.mx
2 Departamento de Ingeniería Química y Metalurgia. Universidad de Sonora. Hermosillo 83000, Sonora, México. Tel: +52 (662) 259-2106; Fax: +52 (662) 259-2105.
Recibido el 19 de octubre del 2001. ]]> Aceptado el 23 de enero del 2002.
Resumen
El escalamiento y optimización de las operaciones cromatográficas de afinidad presenta actualmente un gran interés industrial. Un enfoque que permite ayudar a realizar estas tareas de la ingeniería de bioprocesos, consiste en el desarrollo de modelos matemáticos y el uso de estos modelos en programas de computación, para predecir el comportamiento de estos procesos cromatograficos. En este trabajo, se utilizó un modelo de transporte que incluye la difusión en el poro, la resistencia en la película y una cinética de adsorción finita, para describir matemáticamente el comportamiento de un sistema de adsorción por afinidad en un tanque perfectamente agitado. Como sistema modelo se utilizaron datos experimentales de la literatura que describen la adsorción por afinidad de β-galactosidasa en anti-β-galactosidasa inmovilizada en partículas de sílice porosa. El sistema de ecuaciones diferenciales del modelo matemático fue resuelto utilizando el método numérico de líneas (NUMOL) utilizando el algoritmo de integración Runge-Kutta-Fehlberg. Esta solución fue comparada con una más simplificada obtenida con el modelo de parámetros agrupados. El mejor ajuste a los datos experimentales se obtuvo con la solución del modelo de transporte, sin embargo, el ajuste con el modelo de parámetros agrupados también fue bastante preciso. El uso del modelo de transporte permitió obtener los perfiles de concentración de proteína en el líquido del poro y en la fase sólida del adsorbente. Los pronunciados perfiles de concentración observados en la etapa inicial del proceso de adsorción en ambas fases, mostraron que la velocidad a la transferencia de masa en el sistema experimental era muy alta. Sólo bajo esta condición los resultados del modelo de transporte y del modelo de parámetros agrupados son muy próximos. El uso del modelo de transporte es una forma única para predecir el comportamiento de la adsorción por afinidad en un tanque perfectamente agitado, así como para lograr un mejor entendimiento de los mecanismos fundamentales responsables de las bioseparaciones.
Palabras clave: Cromatografía de afinidad, simulación, modelos matemáticos.
Abstract
The scale-up and optimization of large-scale affinity chromatographic operations is of major industrial importance. The development of mathematical models and their use in computer programs to predict the performance of these chromatographic processes is an approach that can help to perform these bioprocess engineering tasks. In this work, a transport model which include pore diffusion, external film resistance, and finite kinetic rate, was used to mathematically describe the performance of a batch affinity adsorption system. Experimental data from literature describing the adsorption of β-galactosidase onto anti-β-galactosidase immobilized on porous silica was used as a model system. The differential equations system of the mathematical model was solved using the numerical method of lines (NUMOL) with a Runge-Kutta-Fehlberg integration algorithm. This solution was compared with a simpler one, given by the analytical solution of the lumped parameters model. The best fit to the experimental data was obtained with the transport model solution, however, the fit with the lumped parameters model was accurate too. The use of the transport model allowed to obtain the protein concentration profiles in the liquid inside the adsorbent pores and in the solid phase of the adsorbent. The sharp concentration profiles observed during the initial step of the adsorption process in both phases, showed a very high mass-transfer rate in this experimental system. Only under this condition the results using transport model and the lumped parameters model are very close. The use of the transport model is a unique way to predict batch affinity performance as well as to obtain a better understanding of the fundamental mechanisms responsible for the bioseparations.
Keywords: Affinity chromatography, simulation, mathematical models.
]]> Introducción
La cromatografía de afinidad es un método industrial muy utilizado en procesos de purificación de proteínas de alto valor en el mercado como enzimas, hormonas, vacunas, citocinas y anticuerpos monoclonales [1-4]. Recientemente, las operaciones por afinidad también han sido consideradas en la purificación a gran escala de plásmidos de ácido desoxiribonucleico (ADN) para su aplicación en terapia génica y vacunación [5]. Este método cromatográfico es especialmente competitivo en este tipo de procesos donde las moléculas de interés se encuentran presentes a muy bajas concentraciones en fluidos complejos como caldos de fermentación y sueros sanguíneos. Los adsorbentes por afinidad se preparan inmovilizando sobre la superficie del soporte los ligandos que interaccionan específicamente con las macromoléculas de interés. Las moléculas utilizadas como ligandos bioespecíficos o pseudoespecíficos incluyen anticuerpos, proteínas, inhibidores, cofactores, colorantes y iones quelatantes [6-10].
El diseño y optimización de las operaciones de afinidad cromatográfica es de gran importancia industrial [11-14]. El desarrollo de modelos matemáticos para describir el comportamiento de los procesos de afinidad es un enfoque que puede ayudar a desarrollar estas tareas de los ingenieros de bioprocesos [12, 15]. El uso de estos modelos generalmente requiere la determinación experimental de los parámetros asociados mediante experimentación y con el uso de correlaciones matemáticas. Las expresiones obtenidas a través de este enfoque generalmente involucran ecuaciones diferenciales parciales (EDP) no lineales que no presentan una solución analítica. La simulación de los procesos se realiza mediante programas de computación que facilitan la obtención de la solución aproximada del modelo.
Existen varios trabajos reportados sobre la modelación y simulación de procesos de adsorción por afinidad por lotes como los de Chase [16], Arnold et al. [1], Arve and Liapis [17] y Hortsmann and Chase [18]. Sin embargo, actualmente existe una necesidad real del uso de métodos numéricos avanzados para resolver este tipo de modelos, actividad que continua ocupando a muchos ingenieros y científicos.
Existen dos estrategias principales para resolver EDP: el método global y el método de líneas. En el método global se discretizan tanto las derivadas espaciales como las temporales. El método numérico de líneas (NUMOL de sus siglas en inglés) es un enfoque modular para programar la solución de ecuaciones diferenciales. Es un método nuevo que utiliza algoritmos robustos para la solución de ecuaciones diferenciales ordinarias de valor inicial de tipo duro (stiff) [19-20]. La solución de las ecuaciones diferenciales parciales se lleva a cabo en dos pasos: el problema de valor de frontera se resuelve utilizando una técnica de discretización, seguidamente el problema de valor inicial resultante se resuelve utilizando un integrador apropiado. Actualmente, NUMOL es una de las técnicas más utilizadas para resolver ecuaciones diferenciales parciales en escalas de tiempo grandes [21]. No obstante que existen paquetes que utilizan esta metodología para resolver problemas bidimensionales, no es fácil insertar las ecuaciones de adsorción por afinidad en estos paquetes, debido a que la descripción de estos procesos no es exactamente bidimensional sino un modelo de dos regiones [22].
En este trabajo se utiliza un modelo de transporte que considera tres resistencias consecutivas a una separación de equilibrio ideal: resistencia en la película externa del adsorbente, difusión interna en los poros del adsorbente y cinética de adsorción finita; con el propósito de simular el comportamiento de la adsorción de proteínas por afinidad en procesos por lotes. Este tipo de modelos proporciona una descripción general realista de la mayoría de los sistemas de interés práctico [23]. La solución del modelo fue obtenida utilizando el NUMOL. Esta solución fue comparada con la solución analítica del modelo de parámetros agrupados de afinidad por lotes [16, 24], y con datos experimentales de la literatura para la adsorción por lotes de β-galactosidasa en anti-β-galactosidasa inmovilizada en partículas de sílice porosa [17].
Descripción de procesos de adsorción por afinidad por lotes
Gran parte de la información necesaria para evaluar el comportamiento de los procesos de afinidad por lotes, está contenida en las curvas típicas de concentración de soluto vs. tiempo. Estas curvas pueden ser utilizadas para determinar: 1) la capacidad del adsorbente que ha sido utilizada, 2) la cantidad de soluto que no se adsorbe al final de la operación y 3) el tiempo de proceso. Un modelo matemático que pueda ser utilizado para predecir apropiadamente este comportamiento dinámico, proporciona una forma práctica de obviar muchos experimentos para el diseño y escalamiento de procesos de afinidad.
Modelo de transporte
]]> El modelo de afinidad por lotes utilizado en esta investigación, se basa en la adsorción isotérmica de una proteína sobre partículas esféricas de adsorbente de radio promedio, rm, y porosidad, εi. La operación se supone se conduce en un tanque bien agitado con un volumen de sistema V. El volumen de líquido externo a la matriz de adsorbente es εbV y el volumen de adsorbente es (1 - εb)V. La concentración inicial y transiente de proteína en el seno del líquido son co y c(t), respectivamente. La concentración de proteína en el líquido de los poros y en la superficie del adsorbente son ci y qi, respectivamente.Para desarrollar una descripción matemática del proceso cromatográfico de afinidad por lotes, se incorporan tres resistencias a la separación de equilibrio ideal: resistencia en la película, difusión intrapartícula e interacción cinética soluto-ligando. Se considera que el movimiento de soluto involucra su transporte interfacial desde el seno del líquido hasta la superficie del adsorbente a través de una película estancada que rodea al adsorbente caracterizada por un coeficiente de transferencia de masa, kf, la difusión dentro del líquido del poro del adsorbente descrita por un coeficiente, Di, y el paso de adsorción del soluto en los sitios activos sobre la superficie del adsorbente. La velocidad de adsorción intrínseca puede ser descrita por diferentes tipos de modelos. En este trabajo se utiliza un modelo de adsorción-desorción tipo Langmuir.
Debido al equilibrio no lineal que caracteriza a la cromatografía de afinidad, el comportamiento de la adsorción se describe más apropiadamente mediante teorías cinéticas. Este enfoque ingenieril para la obtención de modelos, involucra el uso de ecuaciones de conservación, leyes de equilibrio en interfases y leyes cinéticas de transporte y adsorción, conjuntamente con condiciones iniciales y de frontera.
Para describir el cambio de concentración de proteína con el tiempo, se puede derivar mediante un balance de soluto en el seno del líquido la ecuación siguiente:

La ecuación para describir el cambio de concentración de soluto en el fluido de los poros del adsorbente puede ser obtenida mediante un balance de soluto en la partícula,

Generalmente se utilizan modelos simplificados para describir las complejas interacciones entre el soluto y el adsorbente de afinidad [1,16,18]. En estos modelos se utiliza una expresión cinética reversible de segundo orden, donde se supone que el soluto interacciona en forma monovalente con el adsorbente,
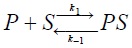
donde: P es el soluto en la solución, S es el sitio de adsorción y PS es el complejo soluto-ligando.
]]> La velocidad de adsorción de este tipo de interacción se representa frecuentemente por la expresión de Langmuir,
donde: qm es la capacidad máxima de adsorción del adsorbente; k1 y k-1 son las constantes cinéticas de adsorción y desorción, respectivamente.
Al inicio de la operación la concentración de proteína en el seno del líquido es co y el sistema se encuentra libre de soluto, por tanto se utilizan las condiciones iniciales siguientes:

Debido a la simetría de la partícula, se considera la condición de frontera siguiente:

Mediante un balance de soluto en la boca de un poro de la partícula, se obtiene una segunda condición de frontera,

Modelo de parámetros agrupados
]]> El modelo de parámetros agrupados [16, 24] utiliza un enfoque empírico sencillo para describir el proceso de adsorción, donde se supone que todos los procesos que limitan la velocidad de adsorción del soluto pueden ser representados por constantes cinéticas. En este enfoque, la velocidad de transferencia de masa de soluto al adsorbente se supone que es descrita por la Ec. (3). En un proceso de adsorción por afinidad en un tanque bien agitado, la concentración de soluto en solución a un cierto tiempo está dada por la siguiente solución analítica del modelo:
donde:

Estimación de parámetros
Un requisito fundamental para el uso de los modelos matemáticos de adsorción por afinidad para predecir el comportamiento, escalar o diseñar un proceso de interés; es la estimación precisa, en forma experimental o mediante correlaciones, de los parámetros asociados al modelo.
Los parámetros que caracterizan el equilibrio del sistema: la capacidad máxima de adsorción, qm, y la constante de disociación de equilibrio, Kd = k-1 / k1, pueden ser estimadas a partir de datos del sistema de adsorción por lotes en equilibrio. El parámetro cinético k1 puede ser calculado de datos de adsorción dinámicos obtenidos en sistemas por lotes o en columnas [16, 18]. El coeficiente de transferencia de masa, kf, puede ser estimado mediante correlaciones empíricas [12]. La difusividad intrapartícula, Di, puede estimarse mediante experimentos de adsorción por afinidad en lotes o en columna de acuerdo a los procedimientos detallados reportados en la literatura [4]. Este parámetro también ha sido estimado en forma precisa utilizando modelos generados para adsorbentes de estructura porosa obtenidos mediante la teoría de redes. Esta teoría representa en forma apropiada la naturaleza discreta de las estructuras porosas de los medios cromatográficos y sirve para describir la difusión restringida dentro del poro [25-27]. En algunos trabajos recientes, la difusividad efectiva dentro del poro ha sido estimada combinando el método experimental de la microscopía laser de escaneo confocal con los modelos matemáticos de adsorción [28-31].
Una vez que los valores de los parámetros que caracterizan los mecanismos de transferencia de masa y de adsorción en el sistema han sido determinados, los modelos matemáticos correspondientes pueden ser utilizados para predecir y estudiar el comportamiento dinámico del sistema bajo diferentes condiciones de diseño y operación.
En este trabajo se seleccionó como sistema modelo la adsorción por afinidad de β-galactosidasa sobre anti-β-galactosidasa inmovilizada en una matriz de sílice porosa y los valores de los parámetros reportados para este sistema por Arve y Liapis [17]. Los datos utilizados para conducir los estudios de simulación se presentan en la Tabla 1.
]]>
Simulación del proceso de afinidad por lotes
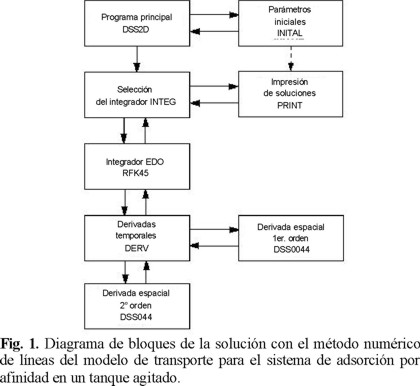
El modelo de transporte para describir la adsorción por afinidad de proteínas en un sistema tipo tanque perfectamente agitado está dado por las ecs.(1-8). Este modelo no tiene una solución analítica y sólo puede ser resuelto mediante técnicas numéricas avanzadas. En este estudio la solución del modelo fue obtenida utilizando el método numérico de líneas NU-MOL de acuerdo al diagrama de bloques que se presenta en la Figura 1. Primeramente, el problema de valor de frontera fue resuelto utilizando las subrutinas DSS004 y DSS044. El problema de valor inicial resultante se resolvió utilizando el integrador de cuarto orden Runge-Kutta-Felhberg RKF45, con una corrección de error de truncación de quinto orden [20]. Estos códigos fueron incorporados en un programa escrito con Fortran 90 que fue corrido en una computadora Digital XP-1000.
Resultados y discusión
La solución del modelo de transporte para la adsorción por afinidad en un tanque perfectamente agitado, de β-galactosidasa sobre anti-β-galactosidasa inmovilizada en una matriz de sílice porosa, fue obtenida utilizando el método numérico de líneas. Esta solución fue comparada con la solución analítica del modelo de parámetros agrupados y con datos experimentales. Estos resultados se muestran en la figura 2 donde se grafica la concentración adimensional de β-galactosidasa en el seno del líquido, c / co, contra el tiempo del proceso de adsorción, t. Las corridas simuladas, tanto con la solución NUMOL como con la del modelo de parámetros agrupados, se ajustan bien a los datos experimentales, con una ligera ventaja del primer método.



En la Fig. 3 puede observarse que el perfil de concentración en el líquido del poro disminuye rápidamente dentro de los 300 minutos iniciales del proceso, hasta alcanzar un valor próximo al equilibrio. Los perfiles de concentración en la fase sólida del adsorbente de la Fig. 4, muestran que la adsorción de proteína se realiza principalmente dentro de esos 300 minutos, después de los cuales estos perfiles permanecen prácticamente inalterados.
Los empinados gradientes de concentración de soluto que se observan en la etapa inicial del proceso de adsorción en ambas fases, sugieren que la velocidad de la transferencia de masa en el sistema es alta. Esto explica la coincidencia de resultados de la simulación de la adsorción de β-galactosidasa con los dos modelos empleados, porque sólo bajo esta condición, como es bien conocido, estos modelos coinciden en sus predicciones.
Conclusiones
La comparación de los resultados obtenidos en las corridas de simulación con el modelo de transporte y con el modelo simplificado de parámetros agrupados, indican que ambos modelos presentan un buen ajuste a los datos experimentales. Sin embargo, la descripción detallada del proceso de adsorción sólo puede ser realizada mediante el uso del modelo de transporte, el cual permite generar los perfiles de concentración que se requieren para el análisis del comportamiento del sistema, o bien mediante análisis paramétricos para determinar la influencia de los principales parámetros de operación.
]]> Los pronunciados perfiles de concentración de soluto que se observan durante la etapa inicial del proceso de adsorción en ambas fases, sugieren que la semejanza en la descripción del proceso de afinidad con ambos modelos obedece a las condiciones particulares del sistema experimental seleccionado, donde la velocidad de transferencia de masa es relativamente alta. En sistemas donde la resistencia a la transferencia de masa sea mayor, el modelo de transporte de tres resistencias puede ofrecer una mejor descripción del comportamiento del sistema.
Notación
co concentración inicial de soluto en el tanque, mg / mL
c concentración de soluto en el seno del líquido, mg / mL
ci concentración de soluto en el líquido de los poros del adsorbente, mg / mL
dp diámetro de la partícula de adsorbente, m
Di difusividad en el poro (difusividad molecular libre / tortuosidad de poro), m2 / s
k1 velocidad específica de adsorción, mL / mg * s
kl1 constante agrupada de adsorción, mL / mg * s
]]> k-1 velocidad específica de desorción, s-1kf coeficiente de transferencia de masa en la película, m / s
Kd constante de equilibrio de desorción, k-1 / k1
P molécula de soluto
PS complejo soluto-sitio activo
qi concentración de soluto en la fase sólida del adsorbente, mg / mL
qm capacidad de adsorción máxima, mg / mL de volumen sólido de adsorbente
qma capacidad de adsorción máxima, mg / mL de volumen de adsorbente
r distancia radial en la partícula de adsorbente, m
rm radio de la partícula de adsorbente, mm
]]> R radio adimensionalS sitio activo
t tiempo, s
V volumen del sistema de adsorción, mL
Letras griegas
εb volumen de solución / volumen total
εi porosidad de la partícula de adsorbente
Agradecimientos
Los autores agradecen el apoyo para la realización de este trabajo a la Universidad de Sonora y al Consejo Nacional de Ciencia y Tecnología de México con el proyecto No. 28295U.
]]>Referencias
1. Arnold, F.H.; Blanch, H.W.; Wilke, C.R. Chem. Eng. J. 1985, 30, B9-B23. [ Links ]
2. Tejeda-Mansir, A.; Montesinos, R.M.; Guzmán, R. Rev. Soc. Quím. Méx. 1995, 39, 166-176. [ Links ]
3. Steinberg, F.M.; Raso, J. Biotech pharmaceuticals and biotherapy. American Council on Science and Health. New York, 1998, pp. 1-31. [ Links ]
4. Liapis, A.I. Sep. Purif. Meth. 1990, 19, 133-210. [ Links ]
]]>5. Ferreira, G.N.M.; Monteiro, G.A.; Prazeres, D.M.F.; Cabral, M.S. Trends Biotechnol. 2000, 18, 380-387. [ Links ]
6. Boschetti, E. J. Chromatogr. A. 1994, 658, 207-236. [ Links ]
7. McCoy, B.J., en: Chromatographic and Membrane Processes in Biotechnology. Acosta, C.A.; Cabral, J.S., Eds., Kluwer Academic Publishers, The Netherlands, 1991, 297-308. [ Links ]
8. Vijayalakshmi, M.A. Trends Biotechnol. 1989, 7, 71-76. [ Links ]
9. Wilchek, M.; Miron, T. Reac. Funct. Polym. 1999, 41, 263-268. [ Links ]
]]>10. Przybycien, T.M. Current Opinion Biotech. 1998, 9,164-170. [ Links ]
11. Liapis, A.I. J. Biotechnol. 1989, 11, 143-160. [ Links ]
12. Kempe, H.; Axelsson, A.; Nilsson, B.; Zacchi, G. J. Chromatogr. A. 1999, 846, 1-12. [ Links ]
13. Fahrner, R.L.; Iyer, H.V.; Blank, G.S. Bioprocess Eng. 1999, 21, 287-292. [ Links ]
14. Tejeda, A.; Noriega, J.A.; Ortega, J.; Guzmán, R. Biotechnol. Prog. 1998, 14, 493-495. [ Links ]
]]>15. A.I. Liapis, A.I.; Unger, K.K., en: Highly Selective Separations in Biotechnology. Steet, G., Ed., Chapman and Hall, Glasgow, N.Z., 1994, pp. 121-162. [ Links ]
16. Chase, H.A. J. Chromatogr. 1984, 297, 179-202. [ Links ]
17. Arve, B.H.; Liapis, A.I. AIChE J. 1987, 33, 179-193. [ Links ]
18. Horstmann, B.J.; Chase, H.A. Chem. Eng. Res. Des. 1989, 67, 243-254. [ Links ]
19. Silebi, C.A.; Schiesser, W.E. Dynamic modeling of transport process systems. Academic Press Inc. San Diego, Ca. 1992. p. 518. [ Links ]
]]>20. Schiesser, W.E.; Silebi, C.A. Computational Transport Phenomena: Numerical methods for the solution of transport problems. Cambridge University Press. Cambridge. U.K. 1997. p. 457. [ Links ]
21. Schiesser, W.E. The numerical method of lines: Integration of partial differential equations. Academic Press. San Diego, Ca. 1991 p. 326. [ Links ]
22. Costa, C.; Rodrigues, A. in: Adsorption: Science and Technology. Rodrigues, A., Ed., Kluwer Academic Publishers, The Netherlands, 1986, pp. 257-265. [ Links ]
23. Skidmore, G.L.; Horstmann, B.J.; Chase, H.A. J. Chromatogr. 1990, 498, 113-128. [ Links ]
24. Ruthven, D.M., Principles of Adsorption and Adsorption Processes, John Wiley & Sons, New York, 1984, pp. 220-273. [ Links ]
]]>25. Smith, G.D. Numerical solution of partial differential equations: Finite difference methods. Oxford University Press. N.Y. Third edition, 1985, p. 345. [ Links ]
26. Meyers, J.J.; Liapis, A.I. J. Chromatogr. A. 1999, 852, 3-23. [ Links ]
27. Meyers, J.J.; Nahar, S.; Ludlow, D.K.; Liapis, A.I. J. Chromatogr. A. 2001, 907, 57-71. [ Links ]
28. Meyers, J.J.; Crosser, O.K.; Liapis, A.I. J. Chromatogr. A. 2001, 908, 35-47. [ Links ]
29. Ljunglof, A.; Thommes, J. J. Chromatogr. A. 1998, 813, 387-395. [ Links ]
]]>30. Kim, H.; Hayashi, M.; Nakatani, K.; Kitamure, N.; Sasaki, K.; Hotta, J.; Masuhara, H. Anal. Chem. 1996, 68, 409-414. [ Links ]
31. Ljunglof, A.; Hjorth, R. J. Chromatogr. A. 1996, 743, 75-83. [ Links ]
32. Ljunglof, A.; Bergvall, P.; Bhikhabhai, R.; Hjorth, R. J. Chromatogr. A. 1999, 844, 29-135. [ Links ]
]]>