
Mejor predictor lineal e insesgado familiar de aptitud combinatoria general en experimentos parciales de cruzas dialélicas con efectos maternos*
Best linear unbiased familiar predictor for partial diallel experiments with maternal effects
Osval Antonio Montesinos–López1§, Ángel Agustín Mastache–Agunas2, Ignacio Luna–Spinoza3, Carlos Moisés Hernández–Suárez4 y Guadalupe Hernández–Lira5
1 Facultad de Telemática, Universidad de Colima. Av. Universidad # 333. Campus Colima. C. P. 28040.
2 Centro de Estudios Profesionales, Colegio Superior Agropecuario del Estado de Guerrero.
]]> 3 Universidad del Istmo–Campus Ixtepec. Cd. Universitaria s/n, 70110, Ixtepec, Oaxaca.4 Facultad de Ciencias, Universidad de Colima. Av. Universidad # 333. Campus Colima. C. P. 28040.
5 Instituto de Socioeconomía, Estadística e Informática, Programa en Estadística, Colegio de Postgraduados. 56230. Montecillo, Estado de México, México.
* Recibido: Noviembre, 2006
Aceptado: Marzo, 2009
§Autor para correspondencia:
oamontes1@ucol.mx.
]]> RESUMEN
En el mejoramiento genético de plantas y animales se han utilizado los experimentos de cruzas dialélicas (diseños completos de Griffing) para realizar estimaciones de parámetros y pruebas de hipótesis, lo cual es importante para la toma de decisiones en programas de mejoramiento genético. Los esquemas completos de Griffing son útiles cuando el número de líneas progenitoras es pequeño, sin embargo, cuando este número es elevado es difícil preparar, establecer y conducir los trabajos de campo. Una alternativa consiste en emplear los diseños parciales de cruzas dialélicas, los cuales ensayan un subconjunto del total de cruzas que es posible formar entre los progenitores básicos. Estos experimentos pueden ser simétricos o asimétricos. Además, es frecuente que los investigadores formen grupos o familias de progenitores, lo que implica considerar la estimación de los efectos del grupo o familia. No obstante, hasta ahora no se ha realizado una investigación para obtener el Mejor Predictor Lineal Insesgado del efecto familiar o de grupo considerando los efectos maternos en experimentos parciales bajo el modelo de efectos mixtos. Por lo que en éste trabajo se derivan los MPLI familiares para aptitud combinatoria general en experimentos dialélicos parciales con efectos maternos, y se realiza un algoritmo computacional en comandos SAS–IML que permite la aplicación de la metodología propuesta.
Palabras clave: aptitud combinatoria general, cruzas dialélicas, experimentos parciales, modelo de efectos mixtos.
ABSTRACT
In plant or animal breeding the experiments with diallel crosses (complete Griffing's designs) have been frequently used to estimate parameters and test hypothesis, which is really important for decision making in breeding programs. Nevertheless, the complete Griffing's designs are useful when the number of parental lines is reduced. With a high number of parental lines is difficult to prepare, stablish and conduct the trials in the field. In this situation a partial diallel experiment is recommended, which can be symetric or asymetric. An option is to use the partial diallel designs, which test a subset from the total number of crosses that is possible to develop among the parental lines. These trials can either be symetric or asymetric. In addition is frequent that researchers conform groups of families or parents that implies the consideration of estimating group or family effects. Nevertheless, so far no research has been conducted to estimate the best unbiased lineal predictor of group or family effect taking into account maternal effects in partial designs under a mixed model. For the above reason, in this research the best unbiased lineal predictor of familias for general combining ability in parcial diallel designs, including maternal effects, are derived, and a computer algorithm in SAS–IML commands that allows for the application of the proposed methodology.
Key words: diallel crosses, general combining ability, mixed effects model, partial diallel experiments.
INTRODUCCIÓN
En el mejoramiento genético de plantas y animales se han utilizado extensamente los experimentos de cruzas dialélicas para realizar estimaciones de parámetros y pruebas de hipótesis. Los diseños de Griffing (1956a, 1956b) sirven para estimar aptitud combinatoria general (ACG), aptitud combinatoria específica (ACE), efectos maternos (EM), efectos recíprocos (ER) y componentes de varianza. Estas estimaciones son importantes en la toma de decisiones de programas de mejoramiento genético. Los esquemas completos de Griffing son útiles cuando el número de líneas progenitoras es reducido, sin embargo, cuando el número de líneas progenitoras es elevado es difícil preparar, establecer y conducir los trabajos de campo. Una solución alternativa consiste en emplear los diseños parciales de cruzas dialélicas, los cuales ensayan un subconjunto del total de cruzas que es posible formar entre los progenitores básicos; proporcionado de esta manera una herramienta más elástica al genetista.
]]> Los experimentos parciales de cruzas dialélicas pueden ser simétricos o asimétricos. Los primeros requieren que cada progenitor se involucre con el mismo número de cruzas; los últimos requieren que al menos uno de los progenitores participe en un número diferente de cruzas. Los más útiles son los que cumplen condiciones de simetría.Algunas soluciones de diseño cuando el número de líneas progenitoras es elevado son las propuestas por Kempthorne y Curnow (1961), Fyfe y Gilbert (1963) y Rojas (1973). Estos autores han abordado el análisis y la estimación de parámetros a partir de un modelo de efecto fijos. Para un modelo de efectos mixtos, Mastache (1999) sugiere derivar los mejores predictores lineales e insesgados (MPLI) mediante la metodología desarrollada por Herderson (1963, 1973), Harville (1976), Harville y Carriquiry (1992) para obtener estimadores insesgados y de mínima varianza.
Adicionalmente, es común que los investigadores formen grupos o familias de progenitores, como lo hacen Cervantes et al. (1999) y Ron et al. (1999), de forma tal que los miembros de cada grupo o familia tienen características similares. Esto implica considerar la estimación de los efectos del grupo o familia. No obstante, hasta ahora no se ha realizado una investigación para obtener el MPLI del efecto familiar o de grupo bajo el modelo de efectos mixtos. En este trabajo se derivan los MPLI empíricos de los efectos familiares en experimentos dialélicos parciales con efectos maternos bajo el modelo de efectos mixtos. Adicionalmente, se proporciona un algoritmo computacional en comandos SAS–IML que permiten la aplicación de la metodología propuesta.
MATERIALES Y MÉTODOS
Modelo lineal de efectos mixtos
En términos matriciales, el modelo lineal de efectos mixtos se representa mediante la forma

donde, Y= vector nxl de observaciones, X= matriz diseño nxf conocida, α = vector fxl de parámetros desconocidos correspondientes a los efectos fijos, Z = matriz diseño nxp conocida, θ = vector pxl no observable de los efectos aleatorios tal que observable de efectos residuales o términos de error tal que  Además, Var(y)= Vσ2e = (ZGZ' + R)σ 2e, E(y) = Xα y G matriz diagonal tal que G = (σ2θ / σ2e ) Ip , donde σ2θ = varianza del término aleatorio θ, σ2θ = varianza de los términos de error, Ip = matriz identidad de orden p, y = R frecuentemente es la matriz identidad de orden n . Con base en el modelo (Ec. 1), Henderson (1963, 1973) desarrolló una técnica para abordar los aspectos aleatorios, derivando para ellos los MPLI.
Además, Var(y)= Vσ2e = (ZGZ' + R)σ 2e, E(y) = Xα y G matriz diagonal tal que G = (σ2θ / σ2e ) Ip , donde σ2θ = varianza del término aleatorio θ, σ2θ = varianza de los términos de error, Ip = matriz identidad de orden p, y = R frecuentemente es la matriz identidad de orden n . Con base en el modelo (Ec. 1), Henderson (1963, 1973) desarrolló una técnica para abordar los aspectos aleatorios, derivando para ellos los MPLI.
Método de Henderson para obtener los MPLI
]]> El método propuesto por Henderson (1963,1973) para obtener los MPLI sobre la base del modelo de efectos mixtos (Ec. 1) supone que en la Ec.1 θ y ε son vestores aleatorios no observables, tales que θ ~ Np(0,Gσ23) y ε ~ Nn(0Rσ23), donde, G y R= matrices no singulares. Henderson (1963, 1973) reporta que la densidad conjunta de θ y y es f(y,θ)= d=(y/θ) c(θ),donde, c(θ )= densidad marginal de θ y d(y/ θ) = densidad condicional de y dado θ En forma explicita f (y, θ) es:

Las siguientes ecuaciones normales del modelo mixto se obtienen maximizando la densidad conjunta (Ec. 2) con respecto a α y θ.
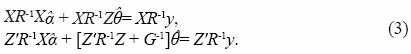
Las soluciones para α, en las ecuaciones normales (Ec. 3), son idénticas a las de mínimos cuadrados generalizados obtenidas de la ecuación  y, donde, V= ZGZ'+R y Var(y)= Vσ 2e , de que en las ecuaciones normales (Ec. 3) no se requiere la inversa de matriz V. De las ecuaciones normales (Ec. 3) se tiene que el MPLI para el vector aleatorio θ es:
y, donde, V= ZGZ'+R y Var(y)= Vσ 2e , de que en las ecuaciones normales (Ec. 3) no se requiere la inversa de matriz V. De las ecuaciones normales (Ec. 3) se tiene que el MPLI para el vector aleatorio θ es:
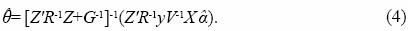
En la mayoría de las aplicaciones, los componentes de varianza involucrados en G y R son desconocidos y deben estimarse a partir de la información experimental. De acuerdo con Harville y Carriquiry (1992), el procedimiento de estimación se divide en dos etapas. En la primera se estiman los componentes de varianza y en la segunda se utilizan estos estimadores, incluyéndolos en las ecuaciones normales (Ec. 3), para obtener el MPLI, llamado MPLI empírico. En esta investigación los componentes de varianza se obtienen por el método derivado del análisis de varianza, cuyas propiedades son descritas por (Robinson, 1991).
En algunas ocasiones, al realizar la estimación de los componentes de varianza con la información correspondiente se obtienen estimaciones negativas, en cuyo caso, Robinson (1991) sugiere considerarlos iguales a cero, aunque esto provoca que los estimadores sean sesgados.
Modelo lineal en experimentos dialélicos
]]> Si se incluyen los efectos maternos, de acuerdo con Martínez (1983 y 1988), el modelo lineal apropiado para el análisis de experimentos dialélicos establecidos en el diseño de bloques completos al azar es:
donde, yijk= valor fenotípico observado de la cruza (i, j) en el bloque k, µ = efecto común a todas las observaciones, gi = efecto de aptitud combinatoria general del progenitor i, sij = efecto de aptitud combinatoria específica de la cruza (i, j), mi= efecto materno del progenitor i , lij= efecto recíproco de la cruza (i, j); δk = efecto del bloque k, y eijk = efecto aleatorio del error correspondiente a la observación (i, j, k). Los términos gi sij, mi, lij y eijk se consideran como variables aleatorias normales no correlacionadas entre y dentro de ellas, con media cero y varianzas σ 2g,σ 2s,σ 2m, σ 2l,σ 2e y respectivamente, con sij= sij y lij= –lji. Si sólo se consideran las medias de las cruzas y se elimina el efecto de bloques, dado que éste es ortogonal con las cruzas, la representación del modelo (Ec. 5) se reduce a:

Si se ensaya un subconjunto t < p2 del total de cruzas posibles a partir de p progenitores, entonces también es posible utilizar el modelo (Ec. 6), el cual se expresará de la siguiente forma:

donde, nij = 1 si la cruza (i, j) participa en el experimento y nij= 0 en caso contrario. Los términos restantes de la Ec. 7 son idénticos a como se definieron en la Ec. 8, con la única diferencia de que ahora son los promedios por bloques.
RESULTADOS
Estimación de los MPLI familiares de ACG y EM
]]> Cuando se ensayan las p(p–1)/2 cruzas directas y las p(p–1)/2 cruzas recíprocas se genera el diseño tres de Griffing, por lo que en este caso t= p(p–1). Cuando se ensayan las cruzas directas, las recíprocas y las p autofecundaciones se tiene el diseño uno de Griffing, por lo que t= p2 . En los experimentos parciales sólo se estudia una fracción del total de cruzas, es decir, t < p(p–1) cuando no se ensayan las autofecundaciones y t < p2 cuando éstas son consideradas en el experimento. Por lo tanto, la derivación analítica de los MPLI familiares de ACG con efectos maternos es similar en ambos casos, con y sin las autofecundaciones, tomando la precaución de generar adecuadamente los elementos matriciales correspondientes.MPLI familiar parcial de ACG
Si en el modelo (Ec. 7) se considera las siguientes igualdades:
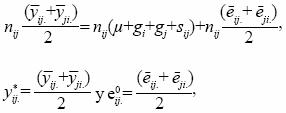
entonces

En notación matricial se tiene que:

donde, y*= un vector txl de observaciones que contiene el promedio de las cruzas observadas, j = vector txl de unos, t= número total de cruzas; µ= escalar que representa el efecto común a todas las cruzas, Zg= matriz diseño de orden txp correspondiente a los efectos de la ACG, g = vector pxl tal que  , s es un vector txl tal que s ~ Nt (0, Rs, σ 2e) y e0 es un vector txl de términos de error tal que e0 ~ Nh(0, Re, σ 2e). Debido a que s y e0 tienen una estructura de covarianzas similar, entonces es factible utilizar la igualdad e*= s + e0, la cual nos conduce a que la Ec. 8 pueda representarse como:
, s es un vector txl tal que s ~ Nt (0, Rs, σ 2e) y e0 es un vector txl de términos de error tal que e0 ~ Nh(0, Re, σ 2e). Debido a que s y e0 tienen una estructura de covarianzas similar, entonces es factible utilizar la igualdad e*= s + e0, la cual nos conduce a que la Ec. 8 pueda representarse como:


donde,  a la matriz identidad de orden p, S= matriz simétrica txt formada por unos en aquellas posiciones en las que la cruza es tal que ij= ji y por ceros en las posiciones restantes, E es una matriz similar a S, diferenciándose de ésta por la presencia de un dos en los casos en que i= j . Las matrices S y E son singulares, esto implica que R* también sea singular, pero, de acuerdo con Harville (1976), si R* es singular en las ecuaciones normales del modelo mixto, entonces R*–1 se sustituye por alguna inversa generalizada R –*. Por lo antes expresado y por la (Ec. 10) se tiene un caso particular del modelo (Ec. 1) en el que n= t, f= 1, p= p y sus componentes son: X= j, α= µ, Z= Zg, θ = g, R= R* y ε = e*. Así, las ecuaciones normales del modelo mixto son:
a la matriz identidad de orden p, S= matriz simétrica txt formada por unos en aquellas posiciones en las que la cruza es tal que ij= ji y por ceros en las posiciones restantes, E es una matriz similar a S, diferenciándose de ésta por la presencia de un dos en los casos en que i= j . Las matrices S y E son singulares, esto implica que R* también sea singular, pero, de acuerdo con Harville (1976), si R* es singular en las ecuaciones normales del modelo mixto, entonces R*–1 se sustituye por alguna inversa generalizada R –*. Por lo antes expresado y por la (Ec. 10) se tiene un caso particular del modelo (Ec. 1) en el que n= t, f= 1, p= p y sus componentes son: X= j, α= µ, Z= Zg, θ = g, R= R* y ε = e*. Así, las ecuaciones normales del modelo mixto son:

Si se conocen los componentes de varianza , σ 2e , σ 2s y σ 2g entonces el MPLI parcial para  se obtiene al resolver el sistema de ecuaciones simultaneas (Ec. 11). Considerando la restricción
se obtiene al resolver el sistema de ecuaciones simultaneas (Ec. 11). Considerando la restricción 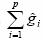 en el sistema de ecuaciones (Ec. 11) se tiene que
en el sistema de ecuaciones (Ec. 11) se tiene que 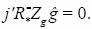 . Por lo tanto
. Por lo tanto 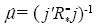 j' R –*y* y el MPLI de ACG es:
j' R –*y* y el MPLI de ACG es:

La Ec. 12 es el MPLI parcial de ACG y tiene la siguiente forma  . Dado que necesitamos estimarlos efectos familiares, esto implica que con los p progenitores se formaran familias o grupos de progenitores. Por ejemplo, supóngase que se cuentan con p =6 progenitores que se agrupan en tres familias: f1={p1, p2}, f2 ={p3, p4}, f3={p5, p6} esto implica que
. Dado que necesitamos estimarlos efectos familiares, esto implica que con los p progenitores se formaran familias o grupos de progenitores. Por ejemplo, supóngase que se cuentan con p =6 progenitores que se agrupan en tres familias: f1={p1, p2}, f2 ={p3, p4}, f3={p5, p6} esto implica que 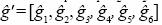 en términos de los efectos familiares es igual a
en términos de los efectos familiares es igual a 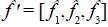 . Por tanto, para el cálculo del efecto de familias también se utiliza la Ec. 12, pero en términos de las familias formadas. Por ello, no es posible simplificar la Ec. 12 y expresarla en términos de las familias porque este número depende del investigador y porque no todas las cruzas estas participando.
. Por tanto, para el cálculo del efecto de familias también se utiliza la Ec. 12, pero en términos de las familias formadas. Por ello, no es posible simplificar la Ec. 12 y expresarla en términos de las familias porque este número depende del investigador y porque no todas las cruzas estas participando.
MPLI parcial de EM
Si en el modelo (Ec. 7) se consideran las siguientes igualdades:
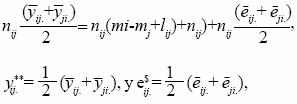
entonces
]]>
En notación matricial se tiene:

donde, y** es un vector txl de observaciones, Zm= a la matriz diseño de orden txp,= a los efectos maternos, m = vector de orden pxl tal que  = a vector de orden txl tal que
= a vector de orden txl tal que  = a un vector txl de términos de error tal que
= a un vector txl de términos de error tal que  . Como l y e$ tienen una estructura de covarianzas similar, entonces es factible hacer e*= l + e$, lo cual nos conduce a que y** pueda representarse como:
. Como l y e$ tienen una estructura de covarianzas similar, entonces es factible hacer e*= l + e$, lo cual nos conduce a que y** pueda representarse como:


donde,  es la matriz identidad de orden p, S* y E* son similares a S y E, con la diferencia de que en S* los unos fuera de la diagonal son negativos y en la matriz E* los términos correspondientes a las autofecundaciones son iguales a cero. Debido a que Rm es singular, se sustituye por alguna inversa generalizada (Harville, 1976). Por lo antes expresado y por la (Ec. 16) se tiene un caso particular del modelo (Ec. 2) en el que n= t, p = p y sus componentes son X= j, Z= Zm, θ= m, R= Rm y ε = e*. Así, las ecuaciones normales del modelo mixto son:
es la matriz identidad de orden p, S* y E* son similares a S y E, con la diferencia de que en S* los unos fuera de la diagonal son negativos y en la matriz E* los términos correspondientes a las autofecundaciones son iguales a cero. Debido a que Rm es singular, se sustituye por alguna inversa generalizada (Harville, 1976). Por lo antes expresado y por la (Ec. 16) se tiene un caso particular del modelo (Ec. 2) en el que n= t, p = p y sus componentes son X= j, Z= Zm, θ= m, R= Rm y ε = e*. Así, las ecuaciones normales del modelo mixto son:

Si se conocen los componentes de varianza σ 2e, σ 2l y σ 2m, entonces el MPLI parcial para se obtiene al resolver el sistema de ecuaciones simultaneas (Ec. 17). Considerando la restricción  = 0 en el sistema de ecuaciones (Ec. 17) se tiene que
= 0 en el sistema de ecuaciones (Ec. 17) se tiene que  . Por lo tanto, el MPLI parcial de EM es:
. Por lo tanto, el MPLI parcial de EM es:

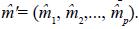 . Como se requieren los efectos familiares de EM, con los p progenitores se formaran familias. De igual forma supóngase que se cuentan con p =6 progenitores que se agrupan en tres familias: f1={p1, p2}, f2 ={p3, p4}, f3={p5, p6} esto implica que
. Como se requieren los efectos familiares de EM, con los p progenitores se formaran familias. De igual forma supóngase que se cuentan con p =6 progenitores que se agrupan en tres familias: f1={p1, p2}, f2 ={p3, p4}, f3={p5, p6} esto implica que  en términos de los efectos familiares es igual a
en términos de los efectos familiares es igual a  . Por tanto, para el cálculo del efecto de familias también se utiliza la Ec. 18, pero en términos de las familias formadas. Esto conduce a que no sea posible simplificar la Ec. 18 y expresarla en términos de familias.
. Por tanto, para el cálculo del efecto de familias también se utiliza la Ec. 18, pero en términos de las familias formadas. Esto conduce a que no sea posible simplificar la Ec. 18 y expresarla en términos de familias. Componentes de varianza
De acuerdo con Martínez (1983), los estimadores obtenidos a través del método de análisis de la varianza para los diseños parciales de cruzas dialélicas con efectos maternos en el que se ensayan t < p2 cruzas o tratamientos son:
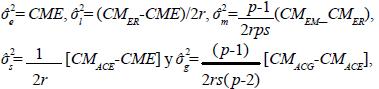
donde, CME es el cuadrado medio del error, CMER es el cuadrado medio del efecto recíproco, CMEM es el cuadrado medio del efecto materno, CMACE es el cuadrado medio de aptitud combinatoria específica y CMACG es el cuadrado medio de aptitud combinatoria general. Sustituyendo σ 2e, σ 2g, σ 2s y en Ec. 12 se obtienen los MPLI empíricos de ACG. De manera similar, sustituyendo σ 2e, σ 2l y σ 2m en la Ec. 18 se obtienen los MPLI empíricos de EM.
Aplicación
A continuación se aplica la metodología propuesta para determinar el MPLI familiar de ACG y de EM en experimentos parciales. Los datos utilizados corresponden a un experimento parcial de cruzas dialélicas (Cuadro 1) en donde se consideran t= 24 cruzas alojadas en dos bloques completos al azar (r= 2). La solución se presenta en forma manual y en forma computacional.
Solución manual
MPLI familiar parcial de ACG
A partir de los datos del Cuadro 1 se tienen los siguientes resultados para valores medios de las cruzas:
]]>
Sustituyendo  , y en la Ec. 12 se tiene que el MPLI parcial de ACG es:
, y en la Ec. 12 se tiene que el MPLI parcial de ACG es:
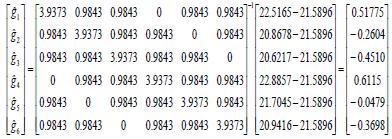
Si los progenitores se agrupan en las siguientes tres familias: f1 = {p1, p2}, f2 = {p3, p4}, f3= {p5, p6} . Reordenando términos se tiene que:

Esto nos conduce a que las ecuaciones normales en términos del efecto familiar son las siguientes:

Finalmente, el MPLI familiar parcial de ACG es igual a:

MPLI familiar parcial de EM
]]> De manera similar, para los valores medios de las cruzas se tiene que:
Utilizando Zm y los datos del anexo 1, Cuadro 1 en la Ec. 18 se tiene que el MPLI parcial de EM es:
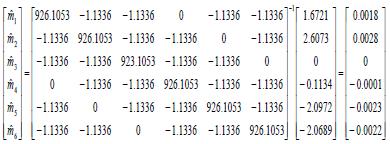
También suponiendo que los progenitores se agrupan en las siguientes tres familias: f1 = {p1, p2}, f2 = {p3, p4}, f3 = {p5, p6}. Así, en términos de los efectos maternos se tiene que:

Resolviendo este sistema de ecuaciones se tiene que el MPLI familiar parcial de EM es:

Solución computacional
Los MPLI familiar parcial de ACG y de EM se pueden obtener con el programa SAS–IML (SAS, 1989) (Anexo 1). Es indispensable, para el uso del algoritmo, que la información colectada en un experimento dialélico parcial se organice de acuerdo al orden y estructura Anexo 1. Además, debe respetarse el nombre del archivo y el orden de las variables especificadas en el comando INPUT debido a que el programa hace uso de ellas. En general, se tendrán t cruzas,donde, I = refiere al progenitor femenino y J al masculino, con I= i, J= j, 1<i, j<p, en DIALELO ij= ji, REP= refiere a las repeticiones r, Y= a la variable respuesta. Las variables IG y JG son muy importantes ya que identifican a los miembros de cada familia por medio de un número entero asignado por el usuario.
]]> El programa SAS–IML produce los resultados que se presentan en los Cuadros 2 y 3, con lo cual se corrobora la metodología descrita anteriormente.
DISCUSIÓN
Los MPLI familiar de ACG y de EM difieren de los estimadores basados en el modelo de efectos fijos por la presencia de las matrices y (Henderson, 1963, 1973; Mastache et al., 1999; Hidalgo et al., 2003; Montesinos et al., 2005) en las Ecuaciones 12 y 18, respectivamente, las cuales involucran los componentes de varianza y afectan a las matrices y , que a su vez hacen que los MPLI de ACG y de EM tengan menor varianza que los obtenidos con el modelo de efectos fijos. La técnica de estimación, desarrollada por Henderson (1963, 1973), para obtener los MPLI tiene mayor precisión que la de mínimos cuadrados generalizados, aún cuando se obtienen los MPLI empíricos. Sin embargo, Harville y Carriquiry (1992) mencionan que existen situaciones en las que la ganancia en precisión ya no es tan grande y los MPLI empíricos deben analizarse con mayor cuidado.
CONCLUSIONES
En esta investigación se obtubierón el MPLI familiar de ACG y de EM en experimentos dialélicos parciales sobre la base del modelo de efectos mixtos con efectos maternos. Además, los MPLI familiares de ACG y de EM, no son necesariamente el promedio de los MPLI de ACG y de EM de los miembros de la familia o grupo, como ocurre en los experimentos de Griffing. Las ecuaciones de estimación de los MPLI familiares parciales de ACG y de EM, son combinaciones lineales de las ecuaciones de estimación de los MPLI parciales de ACG y de EM. Por otro lado, cuando no se conocen los componentes de varianza involucrados en las Ecuaciones 12 y 18, éstos se sustituyen por sus respectivos estimadores y se obtiene el MPLI familiar empírico de ACG y de EM, lo que ocasiona que la precisión del MPLI no sea tan grandes como cuando se conocen los componentes de varianza involucrados. Si éstos son mejores que los obtenidos bajo el modelo de efectos fijos. También es necesario mencionar que los diseños uno y tres de Griffing ocurren como un caso particular de la clase de experimentos dialélicos parciales que consideran efectos maternos. Finalmente, el algoritmo computacional realizado proporciona de una forma rápida y compacta un análisis completo de estimación y predicción de efectos familiares en experimentos parciales de cruzas dialélicas, en donde se involucra la estimación de efectos maternos que considera aleatorios a los efectos de aptitud combinatoria general y específica, efectos maternos y recíprocos, con lo cual se logra un panorama completo de estimación y predicción.
LITERATURA CITADA
Cervantes, S., T; Castillo, G. F. y Domínguez, C. E. 1999. Cambios en la media y en la varianza de caracteres cuantitativos de cebada por irradiación recurrente. Agrociencia 33:251–299. [ Links ]
Fyfe, J. L. and Gilbert, N. 1963. Partial diallel cross. Biometrics 19:287–306. [ Links ]
Griffing, B. 1956a. A generalized treatment of the use of dialell crosses in quantitative inheritance. Heredity 10:31–50. [ Links ]
Griffing, B. 1956b. Concept of general and specific combining ability in relation to dialell crossing systems. Austr. J. Biol. Sci. 9:463–491. [ Links ]
Harville, D. A. 1976. Extension of the Gauss–Markov theorem to include the estimation of random effects. Ann. Statist 4:384–395. [ Links ]
Harville, D. A and Carriquiry, A. L. 1992. Classical and Bayesian prediction as applied to an unbalanced mixed linear model. Biometrics 48:987–1003. [ Links ]
Henderson, C. R. 1963. Selection index and expected genetic advance. pp: 141–163. In: Hanson, W. D. Robinson, H. F. (eds). Statistical genetics and plant breeding. Nat. Acad. Sci., Nat. Res. Council, Publication 982, Washington, D. C. [ Links ]
Henderson, C. R. 1973. Sire evaluation and genetics trends. pp:10–41. In: Proc. Anim. Breed. Genet. Symp. In honor of Dr. Jay L. Lush. Champaign, ILL. [ Links ]
Hidalgo, C. J. V; Martínez, G. A; Mastache, L. A. A y Rendón, S. G. 2003. Mejor predictor lineal e insesgado para aptitud combinatoria general y análisis combinado de los diseños dos y cuatro de Griffing. Rev. Fitotec. Mex. 26 (4):319–329. [ Links ]
Kempthore, O. R. and Curnow N. 1961. The partial diallel cross. Biometrics 17:229–250. [ Links ]
Martínez, G. A. 1983. Diseño y análisis de los experimentos de cruzas dialélicas. Centro de Estadística y Cálculo, Colegio de Postgraduados. Chapingo, Estado de México. p. 345. [ Links ]
Martínez, G. A. 1988. Diseños experimentales. 1a. Edición. Trillas. México. [ Links ]
Mastache, L. A. A; Martínez, G. A y Castillo, M. A. 1999. Los mejores predictores lineales e insesgados (MPLI) en los diseños uno y tres de Griffing. Agrociencia 33:349–359. [ Links ]
Montesinos, L. O. A; Martínez, G. A; Mastache, L. A. A y Rendón, S. G. 2005. Mejor predictor lineal e insesgado para aptitud combinatoria específica de los diseños dos y cuatro de Griffing. Rev. Fitotec. Mex. 28 (4):369–376. [ Links ]
Robinson, G. K. 1991. That BLUP is a good thing: the estimation of random effects. Statistical Science 6(1):15–51. [ Links ]
Ron, P. J; Ramírez, D. J. L; Valdivia, B. R. y Lozano, B. M. 1999. Comparación de tipos de varidades de maíz desarrolladas por el INIFAP en la región Centro–Occidente de México. Agrociencia 33:267–273. [ Links ]
Rojas, B. A. 1973. Design and analysis of diallel crosses. Department of experimental Statistics, New Mexico State University, USA. [ Links ]
Statistical Analysis System Institute. (SAS), Institute Inc. 1989. SAS/IML Software: Usage and Reference, Version 6. Cary, N. C. [ Links ] ]]>