Genes que estimulan las transcripciones en el ámbito nuclear.
Genes de factores de crecimiento o sus receptores.
Genes de proteínas de señales intracitoplasmáticas.
Algunos oncogenes se sobreexpresan en varios tipos de neoplasias como el K-ras y N-ras; el erb-B-2, el c-myc el c-fos y otros. El oncogen -erbB2, se encuentra activado en el 30% de los cánceres mamarios y relacionado con mayor agresividad tumoral, mayor compromiso axilar y menor sobrevida.11
Otros genes pueden participar en la carcinogénesis codificando proteínas que en forma indirecta estimulan la proliferación celular, al interferir con los mecanismos de "freno" regulatorio, tal es el caso del gen bcl2 (ya mencionado más arriba) cuya proteína bloquea el "suicidio" celular, que constituye un mecanismo de defensa cuando la célula acumula numerosas mutaciones.
Los genes supresores son los encargados de contrarrestar a los anteriormente descritos, cumplen su función de dos "maneras claves": a) Frenando las ciclinas y dejando más tiempo a las células en fase G1, para dar oportunidad a los mecanismos de reparación del genoma y b) Induciendo a la apoptosis o "muerte celular programada",12 considerando que la célula debe morir antes que reproducirse con las fallas genómicas. El primer antioncogén descrito fue el del retinoblastoma, que se encuentra en el cromosoma 13, la proteína mutada de este gen se ha vinculado a cánceres de hueso, pulmón, mama y vejiga.
A fines de la década de los ochenta, otra proteína, la p53,9, 14 producto de un gen que se encuentra en el brazo corto del Cr 17, fue designado como "guardián del genoma" que actúa frenando las ciclinas y facilitando la apoptosis. La proteína mutada, por lesiones en el gen que la codifica, fue detectada en más de 50% de todas las neoplasias malignas. Pero existe un hecho paradójico, cuando se detecta dicha proteína p53 en células o en plasma sanguíneo, la misma corresponde a la variante mutada que se comporta con acciones totalmente opuestas a la variante normal (o salvaje) y por ende sudetección corresponde a un signo de mal pronóstico.
La mayoría de los genes supresores son recesivos, es decir que comprometen un alelo (materno o paterno) proveniente de la línea germinal. Se nace con ese defecto y a lo largo de la vida se puede producir la mutación somática del otro alelo y desencadenarse la neoplasia.2,15
Carcinogénesis
Conceptos generales. Mecanismos genéticos y epigenéticos
Lo expuesto anteriormente, anticipa de alguna manera algunos de los mecanismos intrínsecos celulares que podrían estar afectados en el proceso de la carcinogénesis.2,12
]]> Para que una célula normal cambie su fenotipo y se convierta en una célula neoplásica se requieren varias mutaciones en varios genes y eso ocurre a través de mucho tiempo, a veces de años, de estar expuesto a un agente carcinogenético.El cáncer comienza en una célula, es decir que es de origen monoclonal. Esa célula alterada escapa a los controles que anteriormente habíamos mencionado y se vuelve "anárquica", iniciando una generación de más "células anárquicas" que a su vez pueden inducir a cambios similares en las células vecinas.2,3,10
Pero no sólo afectan a la célula las mutaciones inducidas por los carcinógenos, sino que a lo largo de cada división celular (recordemos que pueden llegar a 50 divisiones) se producen errores espontáneos7 en cada duplicación y los mismos se van acumulando constituyendo un factor intrínseco de riesgo; aquí vale la pena señalar que los radicales libres son productos normales del metabolismo celular, pero un exceso de los mismos puede acarrear efectos genotóxicos16 por lo que toma vigencia el valor de los suplementos dietarios con antioxidantes.
La mutación genética conduce a la modificación de los productos que codificaría el gen normal y en la vía de la carcinogénesis darán origen a:
a) Los cánceres heredables por mutaciones en uno o ambos alelos de las células germinales. El análisis citogenético ha permitido individualizar algunos genes cuyas mutaciones han demostrado ser de predisposición familiar.15, 17
b) Los cánceres esporádicos, donde las alteraciones genéticas dependen de los mutágenos ambientales (virus, radiaciones o sustancias químicas).18-20
En la predisposición no heredable, la mutación de algunos genes conduce a consecuencias metabólicas que podría significar una ruta hacia la carcinogénesis.21
El 80% de los cánceres esporádicos se deben a exposición ambiental,22 esto sustentado por la gran cantidad de carcinógenos químicos y físicos existentes y los distintos tipos de cánceres que promueven. Por ejemplo: el cigarrillo predispone al cáncer de pulmóny de vejiga; las aminas aromáticas al cáncer de vejiga; la aflatoxina al cáncer de hígado; el benceno a las leucemias.
Los carcinógenos químicos pueden actuar como inhibidores o activadores de enzimas que a su vez podrían facilitar la acción de esos carcinógenos en el daño genómico y activar algunos oncogenes.22
]]> En la dieta diaria se ingieren diferentes tóxicos y mutágenos y los organismos han desarrollado un sistema de adaptación relacionado a su capacidad individual de detoxificación.Cabe señalar que existen dos mecanismos por los cuales los genes pueden alterarse:
a) Genético, donde se producen alteraciones estructurales del genoma por cambios en la disposición de los propios genes o de sus bases, como ser las mutaciones, translocaciones o deleciones.
b) Epigenético en acciones moleculares por alteraciones de las enzimas o de los sustratos de las mismas, tal el caso de la metilación de las bases.12Este mecanismo generalmente compromete simultáneamente los dos alelos y la hipometilación conduce a la mayor expresión de los genes, por lo tanto, una mayor cantidad de la enzima metiltransferasa que inhibe la metilación puede conducir a la mayor expresión de oncogenes. Esta enzima se encuentra elevada en los tejidos tumorales.
Para una mejor comprensión de los mecanismos epigenéticos deben tenerse en cuenta tres enzimas que juegan un rol importante en la susceptibilidad al cáncer: citocromo p 450 mono-oxigenasa; glutatión-transferasa y acetil-transferasa. No nos referiremos a sus acciones moleculares, considerando que ese aspecto escapa a la intención genérica de este trabajo.23-26
Mecanismos moleculares de defensa
La célula expuesta a tantos factores que pueden dañar el genoma cuenta sin embargo con mecanismos de defensa, de los cuales depende la normal replicación celular. Ya hemos mencionado algunos de ellos, pero consideramos de interés insistir sobre los mismos:
La apoptosis, o muerte celular programada
]]> Las proteínas anticiclinas que "enlentecen" el ciclo celular y dan tiempo a actuar a los mecanismos reparadores del genoma.Las proteínas del complejo NER (del inglés nucleotide excision repair) también denominadas MMR (del inglés mismatch repair genes) que localizan los sectores dañados, devanan la hélice, excluyen el segmento de ADN afectado e incorporan las secuencias correctas.
El acortamiento fisiológico de los telómeros.
Los telómeros son secuencias del genoma que se encuentran en los extremos de los cromosomas y no se ha constatado hasta ahora que codifiquen señales de proliferación. Impiden la pérdida y alteración espontánea de las secuencias de ADN y al mismo tiempo son marcadores del envejecimiento celular, puesto que se van acortando con cada división y llega un punto en que ellos mismos inducen el "suicidio" de la célula.27-31
Cuando los telómeros son "repuestos" por acción de la enzima telomerasa, no llega ese final conveniente para el porvenir del "clon", de ahí, que la sobreexpresión de telomerasas, constituya un signo desfavorable, lo cual se ha demostrado en los tejidos neoplásicos. Esta enzima repara los telómeros mediante la adición de secuencias de las bases TTAGGG.32
Sin embargo, esta enzima puede estar aumentada también en células normales que requieren reproducción activa útil, como son las germinales y algunas hematopoyéticas.33 La telomerasa posee una subunidad proteica designada como TERT, que promueve al ARN con la reposición del ADN telomérico, llevando a la inmortalidad celular.
La unidad proteica TERT de la telomerasa, se sobreexpresa en el cáncer.27, 34 La depleción del ARN de la telomerasa inhibe rápidamente el desarrollo de la célula neoplásica.32,34
Se supone que el telómero "secuestra" proteínas de reparación del genoma, (BRCA1-BRCA2, complejo RAD 50 y otros) para estabilizar su propia estructura.27 No obstante se realizan estudios sobre la acción de las proteínas Hsp 90 y p53, que podrían inhibir la telomerasa.
Las investigaciones sobre esta enzima y la posibilidad de hallar blancos terapéuticos para su inhibición, ha permitido a tres científicos obtener el Premio Nobel de Medicina 2009, ellos fueron: Elizabeth Blackburn, Carol Greider y Jack Szostak.
Conceptos sobre genoma, transcriptoma y proteoma23,24,26
]]> El avance en las investigaciones sobre el tema de la carcinogénesis ha permitido a los científicos concretar conceptos sobre las distintas etapas de la transformación neoplásica y comprender la dinámica en los cambios moleculares, lo que implica la posibilidad de obtener recursos para el diagnóstico y eventuales dianas terapéuticas para la interrupción de todo el proceso neoplásico. Señalaremos brevemente los alcances que definen estos tres aspectos de la investigación molecular (cuadro I).
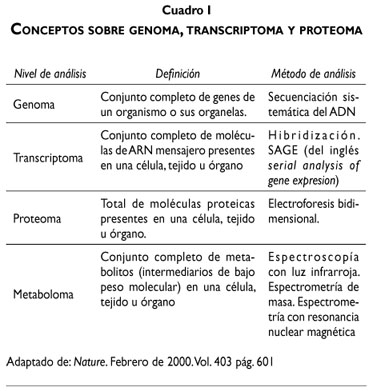
Genoma
El Proyecto ENCODE pretende identificar los elementos funcionales del genoma humano, incluyendo los reguladores de la expresión de los genes, la estructura de la cromatina y los lugares de interacción de los aminoácidos del ADN.13
El cambio de un solo nucleótido significa que puede inducir la iniciación o progresión de la enfermedad neoplásica en el tema que nos ocupa. Otra variabilidad genética que puede cambiar el fenotipo normal a maligno son las deleciones, duplicaciones y amplificaciones génicas ya identificadas por los investigadores científicos.23,26,35,36
Transcriptoma
]]> Está representado por los ARN mensajeros, moléculas que transportan el código del gen, para la síntesis de proteínas.23Los ARNm son miles de moléculas sintetizadas por las ARN polimerasas, y en caso de generarse ARNm anómalos, el resultado será la formación de una proteína anormal. Se ha constatado la existencia de ARNm con acoplamientos anómalos en distintos tipos de cáncer.24
El uso de microchips, permite el análisis de lo transcrito, obteniendo datos cualitativos y cuantitativos en diferentes fases de la vida celular.23
Proteoma
Comprende el reconocimiento de las proteínas que comparten la responsabilidad de la estructura y función celular. Es decir, que la diferencia entre una célula normal y una neoplásica radica en el tipo y cantidad de proteínas que cada una elabora.25,26,37
Las posibles aplicaciones clínicas en el estudio del proteoma serían su contribución al diagnóstico, pronóstico y tratamiento del cáncer, obteniéndose muestras en suero o plasma sanguíneo. Se utilizan métodos extremadamente específicos como las técnicas de espectrometría de masas.24
El análisis del proteoma es más complejo que el del genoma, puesto que éste último se basa en las combinaciones de cuatro aminoácidos, en tanto el proteoma evalúa las proteínas compuestas por 20 aminoácidos diferentes, por lo que las variaciones son mayores.
Etapas de la carcinogénesis y acción de los carcinógenos
Estos pueden actuar en una o en las tres etapas de la carcinogénesis que son: iniciación, promoción y progresión.
La iniciación ocurre a nivel del genoma y las alteraciones pueden darse en los tumores benignos y malignos, al igual que la segunda etapa, pero la tercera, o sea la de progresión, es exclusiva de la transformación maligna. Los agentes que actúan en la primera etapa pueden ser físicos, quimícos o virales.2
]]> Los carcinógenos físicos están constituidos por las radiaciones que dañan, ionizando las bases, deprimen el gen de la proteína p53, pueden estimular citoquinas como la IL 1 y 6, que actúan como verdaderos factores de crecimiento, facilitan la formación de radicales libres y pueden lesionar el gen que codifica para el complejo mayor de histocompatibilidad (CMH) el cual se encuentra en el Cr 6.10Las fuentes radiantes pueden surgir de la metodología diagnóstica o terapéutica como así también por exposición a los rayos solares en forma persistente o por emanaciones de radón de los suelos.22
Los carcinógenos químicos tienen como blanco preferencial al nitrógeno de la guanina (alquilantes, aminas aromáticas, nitrosaminas y grasas poliinsaturadas) produciendo mutaciones irreversibles.
La aflatoxina (aislada de alimentos contaminadoscon un tipo de hongo) se considera oncogénica para lacélula hepática. Se atribuyen efectos genotóxicos a los compuestos policlorados contenidos en insecticidas y plaguicidas, así como también productos de la manufactura de materiales eléctricos y plásticos formandoparte de los contaminantes ambientales que llegan a los seres vivos a través del aire, del agua y de los alimentos.22
Los carcinógenos virales actúan introduciendo sus propias oncoproteínas al genoma de la célula afectada con lo que la misma cambiará su código normal por el que le imponen los oncogenes virales. Tal es el caso del virus papiloma humano,20 del Epstein Bar38 y de las hepatitis B y C.
Los oncogenes virales se ubican generalmente en las proximidades de proto-oncogenes o de oncogenes supresores, activando a los primeros y desactivando a los segundos.18-20, 38
La promoción representa la etapa de crecimiento tisular con la formación del tumor. Participan los factores de crecimiento y los receptores a los factores de crecimiento, como así también la angiogénesis y degradación de las matrices extracelulares.39-41
Los factores de crecimiento (FC), son péptidos producidos por las mismas células o por las vecinas y actúan como facilitadores de la mitosis incorporando en fase S a algunas células que se encuentran en fase G0 o G1 prolongada.
Los FC se sintetizan en una célula y luego migran al espacio intercelular, ejerciendo sus acciones sobre las células vecinas.40-42 Los primeros FC descubiertos fueron el de crecimiento neuronal (NGF) y el epidérmico (EGF), a los que se sumaron muchos más, entre ellos el derivado de plaquetas (PDGF), el de hepatocitos (HGF), el de crecimiento de fibroblastos (FGF) el estimulante de crecimiento de colonias, el símil insulina IGF-1.
Algunas hormonas ejercen acciones similares a estos factores peptídicos una vez que fueron captadas por los receptores de membrana o intra-citoplasmáticos. Es reconocido el efecto proliferativo de los estrógenos sobre los epitelios mamarios y del tracto genital; las gonadotrofinas hipofisarias estimulan especialmente al epitelio ovárico; la prolactina ejerce su acción en el ámbito de la mama y también del ovario; la insulina de origen pancreático y el factor símil insulina, de origen hepático, son verdaderos factores de crecimiento.43, 44
]]> Los receptores de membrana son compuestos glucoproteicos que se unen a los factores de crecimiento y transmiten los mensajes proliferativos por intermedio de sus conexiones transmembrana. Algunas veces, la sobreexpresión de estos receptores los hace autoinducibles, es decir, que se encuentran en acción permanente aún en ausencia del factor de crecimiento.Algunas citocinas que son productos de distintostipos de células pueden ejercer efectos modulatorios o inhibitorios de la proliferación; tal es el caso del factor TGF beta, del interferón y del TNF o factor de necrosis tumoral que antagonizan a los factores de crecimiento.
La progresión implica la capacidad de invadir tejidos vecinos o a distancia, por parte de la célula tumoral maligna. Esa capacidad está codificada también en los genes de la misma con modificaciones estructurales y funcionales.2
Las células normales se encuentran "ancladas" en un hábitat que les es propio. El contacto con las células vecinas controla su propia división celular y existen moléculas de adhesión que las mantienen próximas y permiten la transmisión de señales de una a otra; las células normales son incapaces de atravesar la membrana basal que las separa del tejido conjuntivo sub-basal de donde obtienen los materiales que las nutren; tampoco tienen capacidad de introducirse a los capilares sanguíneos o linfáticos, aunque los linfocitos hacen excepción a esta particularidad.
El proceso metastásico
Angiogénesis
Las células neoplásicas, como hemos señalado, tienen incrementado su metabolismo y por ende requieren de mayor aporte de oxígeno; en las mismas existen genes que codifican factores que estimulan la angiogénesis tumoral, que es el primer requisito necesario para iniciar la cascada metastásica.39
Existen más de 15 factores angiogénicos y otros 15 que frenan dicho proceso. Entre los primeros, una fuente importante involucra a las células endoteliales, que lógicamente abundan en los vasos neoformados. Se estima que entre 5 y 10% de la población celular tumoral está constituida por células endoteliales.
El factor de crecimiento derivado de plaquetas PDGF participa además en los mecanismos de quimiotaxis, es decir facilitan la migración hacia y desde el torrente vascular de las células, sean estas neutrófilos, macrófagos o bien células neoplásicas; por otra parte las células endoteliales "nuevas" liberan unas seis proteínas que estimulan la proliferación celular y la motilidad de las células tumorales.40,41
]]> Los vasos neoformados tienen paredes porosas que les permiten la entrada y salida de las células neoplásicas, todo lo cual se acompaña de la mayor liberación de proteinasas que degradan la matriz extracelular, permitiendo la migración de las mismas.Recientes estudios demostraron que el óxido nítrico estimula la angiogénesis. Pero así como existen substancias angiogénicas también existen substancias angiostáticas elaboradas por el mismo tumor. Lo fundamental de esta etapa de progresión, es comprender las dificultadesque debe superar la célula maligna para colonizar en un lugar distante de su sitio de origen. Baste saber que sólo una célula de entre diez mil que logren introducirse al torrente sanguíneo o linfático podrá asentarse para desarrollar un foco metastático, para lo cual:
a) La célula maligna debe desprenderse de sus vecinas y "navegar" por el espacio intercelular y atravesar la membrana basal (degradación de matrices)
b) Debe introducirse al vaso sanguíneo o linfático (migración celular)
c) Debe sobrevivir al ataque de la respuesta inmune (respuesta inmune)
d) Debe atravesar nuevamente la pared vascular y "anidar" en otro tejido que muchas veces no com parte su estirpe (colonización metastásica)
Haremos una rápida síntesis de cuáles son los mecanismos (conocidos hasta el momento) de los que se vale la célula atípica para vencer tales dificultades.
Degradación de matrices
Las células neoplásicas producen unas colagenasas llamadas metaloproteinasas, que degradan la matriz intercelular, la membrana basal y son capaces de "horadar" las paredes de los capilares sanguíneos y linfáticos.45,46 Por otra parte existen otras sustancias codificadas por las células normales que se denominan TIMP (1 y 2) que significan inhibidoras de las metaloproteinasas.
]]> Además de las metaloproteinasas debe mencionarse el plaminógeno, cuyo efecto es activar la plasmina que disuelve la fibrina y se encuentra en las matrices extracelulares. Todas estas proteasas degradan también la fibronectina y laminina de la membrana celular y se encuentran elevadas en distintos tumores malignos.46Migración celular
En el citoplasma celular existen dos moléculas: la actina y la miosina que producen movimientos intra-citoplasmáticos constantes y por esa misma actividad permiten a la célula "desplazamientos" en los espacios extracelulares de propulsión y retropulsión, tipo "oruga".42
Participan también las moléculas de adhesión de transmembrana: integrinas y cadherinas que fijan las células al sustrato que le servirá de "transporte" como puede ser la fibronectina.
Respuesta inmune
Las células malignas pueden "burlar" la vigilancia inmunológica por la gran cantidad de antígenos que estas poseen, lo cual no daría tiempo al reconocimiento por parte de los responsables de la RI, además puede existir una "falla" a nivel del complejo mayor de histocompatibilidad clase I (CMH-I) por falta de una proteína B 7, que es necesaria para que la presentación sea correcta por parte de dicho complejo a los linfocitos citotócicos (CD8). Las células neoplásicas indiferenciadas carecen generalmente del CMH.
Son numerosos los mecanismos implicados en esta "tolerancia inmunológica", por lo que más adelante haremos una breve referencia a los mismos.
Colonización metastásica
En cuanto a la capacidad de "insertarse" en un tejido que muchas veces no comparte su estirpe, se mencionan actualmente, ciertos factores denominados "prefijo postal", basándose en la teoría de dos investigadores, Dreyer y Leroy Hood, quienes postulan la hipótesis que las células presentan en su superficie ciertas moléculas que son "leídas" por otras células vecinas o situadas a distancia que actúan como moléculas de adhesión.42,45 Esto permitiría explicar cierta selectividad de algunos cánceres para depositar sus metástasis (próstata y mama, en huesos) aunque algunos órganos serían también fácil asiento de metástasis por su particular disposición microcapilar, que facilita el estasis circulatorio y el "anclaje" de la célula neoplásica (pulmón e hígado).
Recientemente se ha dado a las moléculas de adhesión un papel fundamental en todas las etapas de "migración" celular que caracteriza a las células neoplásicas y a otras células normales, tal es el caso de los leucocitos, macrófagos y otras células de la RI.
]]>Inmunidad y cáncer
Se mencionó más arriba que las células tumorales, para su migración, también deben contrarrestar los efectos de la respuesta inmune, pero escapa a los fines de esta monografía efectuar una descripción detallada de esos mecanismos involucrados en la enfermedad neoplásica.
El sistema inmune de los seres vivos es sumamente complejo y especialmente en la escala animal, que es la que nos interesa en relación a este tema, debemos mencionar que tanto los componentes de la inmunidad celular (linfocitos, macrófagos y células presentadoras de antígenos), como la humoral (inmunoglobulinas y citoquinas) mantienen una relación estrecha para el correcto cumplimiento de sus funciones (reconocer lo propio de lo no propio).47-50
Merece un párrafo especial tener en cuenta a los antígenos de histocompatibilidad o HLA, que inducen y regulan la RI. Su función principal consiste en unirse a los fragmentos peptídicos de las proteínas extrañas formando un complejo antigénico intracelular para exponerlas a través de la membrana a las células T de la inmunidad celular.
Existen varios genes que codifican estos antígenos de histocompatibilidad agrupados en el Cr 6, este complejo es muy polimórfico y sus productos constituyen tres sistemas: clase I, clase II y clase III.
El HLA tipo I se encuentra en todas las células (menos en los eritrocitos, espermatozoides y células amnióticas) y se encarga de regular el procesamiento y presentación de los antígenos endógenos para ser presentados en la superficie celular al receptor del linfocito CD8 citotóxico; para que el HLA cumpla dichas funciones se requiere la presencia de un péptido B7; dicha molécula puede estar ausente en células neoplásicas, lo que explicaría una de las causas de la "tolerancia" inmunológica en estas enfermedades.
El HLA tipo II se encuentra en las células T activadas (T4) células B y macrófagos. El tipo de Ag a los que se asocian para su presentación, son de naturaleza distinta puesto que se trata de Ag exógenos (microbios extracelulares, proteínas solubles) que previamente son procesados en la misma célula por los lisosomas. La molécula de clase II se une al receptor CD4 del linfocito helper y presenta antígenos solubles de superficie.
En algunos cánceres humanos se han demostrado antígenos específicos del tumor y otros que se expresan en varios tumores y que representan el "resurgimiento" de antígenos silenciados durante el desarrollo y diferenciación de los tejidos.
Merece una consideración especial una molécula no clásica del HLAI, denominada HLA-G, inicialmente descubierta en la década del noventa, en el citotrofoblasto en la mujer embarazada y que participa evitando el rechazo embrio-fetal, inhibiendo el sistema inmune.51
]]> Posteriores estudios, demostraron que dicha molécula también fue detectada en diversos tejidos neoplásicos y en sueros de pacientes con algunas infecciones virales, incluso en el sida.52El escape tumoral a la respuesta inmune y la identificación del HLA-G ha sido informado por diversos autores demostrando que dicha molécula inhibe a los interferones beta y gamma, como así también a los linfocitos CD4 y CD8.47
Consideración final
Condensar en esta monografía una revisión parcial bibliográfica actualizada, y luego evaluarla, nos produjo la sensación de cuán poco transmitimos en ella y cuán mucho queda por trabajar en este nuestro entusiasmo por conocer, de "segunda mano", aquello que es privilegio de quienes en la investigación creativa dan luz a los misterios de la vida y de los mecanismos que pueden comprometerla.
Nos parece oportuno transcribir: "Algún día tal vez saldrá a la luz una de las ironías de la naturaleza: ... que el cáncer, responsable de muchas muertes, está conectado muy indisolublemente con la vida"
C.Oberling- 1946
Declaración de conflicto de intereses: Los autores declararon no tener conflicto de intereses.
]]>Referencias
1. Blanco J, Bullón M. Cuadernos de genética. España: Marban, 1987. [ Links ]
2. Cavenee WK,White RL.The genetic basis of cancer. Sci Am 1995;272(3):72-79. [ Links ]
3. Estevez R. Oncología Clínica. El Salvador: Edic. Univ., 1978. [ Links ]
4. Celada A. Factores de transcripción y control de la expresión génica. Investig Cienc 1991;179:42-52. [ Links ]
]]>5. Bergers E, van Diest PJ, Baak JP. Cell cycle analysis of 932 flow cytometric DNA histograms of fresh frozen breast carcinoma material. Correlations between flow cytometric, clinical, and pathologic variables. MMMCP Collaborative Group. Multicenter Morphometric Mammary Carcinoma Project Collaborative Group. Cancer 1996 1;77(11):2258-2266. [ Links ]
6. Moreno S. Comienzo de mitosis. Investig Cienc, 1992;187:62-70 [ Links ]
7. Radman,Wagner R. Fidelidad de la duplicación del ADN. Investig Cienc 1988;145:20-30. [ Links ]
8. Arango MC, Llanes L, Díaz T, Faxas ME. La apoptosis: sus características y su papel en la transformación maligna de la célula. Rev Cubana Oncol 1997;13(2):126-134. [ Links ]
9. Weinberg RA.The molecular basis of oncogenes and tumor suppressor genes.Ann N Y Acad Sci 1995;758:331-338. [ Links ]
10. Cohen SM, Ellwein LB. Genetic errors, cell proliferation, and carcinogenesis. Cancer Res 1991;51(24):6493-6505. [ Links ]
11. Michelin S. El oncogén c-erbB2 (neu/Her-2) y su expresión en el cáncer de mama humano. Revista Latinoamericana de Mastología1997;1(3):181-190 [ Links ]
12. Laird PW. Oncogenic mechanisms mediated by DNA methylation. Mol Med Today 1997;3(5):223-229. [ Links ]
13. Margulies EH, Cooper GM,Asimenos G,Thomas DJ, Dewey CN, Siepel A, et al. Analyses of deep mammalian sequence alignments and constraint predictions for 1% of the human genome. Genome Res 2007;17(6):760-774. [ Links ]
14. Perry ME, Levine AJ.Tumor-suppressor p53 and the cell cycle. Curr Opin Genet Dev 1993;3(1):50-54. [ Links ]
15. Cramer DW, Muto MG, Reichardt JK, Xu H,Welch WR,Valles B, et al. Characteristics of women with a family history of ovarian cancer. I. Galactose consumption and metabolism. Cancer 1994;74(4):1309-1317. [ Links ]
]]>16. Romero MP. Cáncer y Metástasis, relación con radicales libres. Oncología1993;3(3):79-94. [ Links ]
17. Narod SA. Hereditary Breast Carcinoma Syndromes.Workshop on Heritable Cancer Syndromes and Genetic Testing. Supplement to Cancer 1997;537-541. [ Links ]
18. Gallo R. Virus oncogénicos ARN. Seminarios de Oncología 126-148. Buenos Aires: Editorial Médica Panamericana, 1977. [ Links ]
19. Green M. Virus ADN: replicación, expresión del gene tumoral y papel en el cáncer humano. Seminarios de Oncología 103-125. Editorial Médica Panamericana. Buenos Aires, 1977. [ Links ]
20. Iwasawa A, Nieminen P, Lehtinen M, Paavonen J. Human papillomavirus DNA in uterine cervix squamous cell carcinoma and adenocarcinoma detected by polymerase chain reaction. Cancer 1996;77(11):2275-2279. [ Links ]
]]>21. Wolf CR. Metabolic factors in cancer susceptibility. Cancer Surv 1990;9(3):437-474. [ Links ]
22. León J, Guerrero I, Pellicer A.Activación de los oncogenes por radiación y agentes químicos. Investig Cienc 1988;143:20-34. [ Links ]
23. Liu ET. Genomic technologies and the interrogation of the transcriptome. Mech Ageing Dev 2005;126(1):153-159. [ Links ]
24. Rhodes DR,Yu J, Shanker K, Deshpande N,Varambally R, Ghosh D, et al. Large-scale meta-analysis of cancer microarray data identifies common transcriptional profiles of neoplastic transformation and progression. Proc Natl Acad Sci USA 2004;101(25):9309-9314. [ Links ]
25. Jensen ON. Modification-specific proteomics: characterization of posttranslational modifications by mass spectrometry. Curr Opin Chem Biol 2004;8(1):33-41. [ Links ]
]]>26. Pastwa E, Somiari SB, Czyz M, Somiari RI. Proteomics in human cancer research. Proteomics Clin Appl. 2007;1(1):4-17. [ Links ]
27. Greider CW.Telómeros, telomerasa y cáncer. Investig Cienc 1996; 20-26. [ Links ]
28. Blackburn EH. Structure and function of telomeres. Nature 1991;350(6319):569-573. [ Links ]
29. Feng J, Funk WD,Wang SS,Weinrich SL,Avilion AA, Chiu CP, et al. The RNA component of human telomerase. Science 1995;269(5228):1236-1241. [ Links ]
30. Kim NW, Piatyszek MA, Prowse KR, Harley CB,West MD, Ho PL, et al. Specific association of human telomerase activity with immortal cells and cancer. Science 1994;266(5193):2011-2015. [ Links ]
]]>31. Perez M, Dubner D, Michelín S, Gisone P, Carosella E.Telómeros y reparación de daño genómico: Su implicancia en patología humana. Medicina (B.Aires) 2002;62(6):593-603. [ Links ]
32. Li S, Crothers J, Haqq CM, Blackburn EH. Cellular and gene expression responses involved in the rapid growth inhibition of human cancer cells by RNA interference-mediated depletion of telomerase RNA. J Biol Chem 2005;280(25):23709-23717. [ Links ]
33. Maschioveccho V.Telomerasa: nuevo marcador tumoral. Departamento Inmunología y Genética. Buenos Aires: Inmunología IACA, 2007. [ Links ]
34. Li S, Blackburn EH. Expression and suppression of human telomerase RNA. Cold Spring Harb Symp Quant Biol 2006;71:211-215. [ Links ]
35. Redon R, Ishikawa S, Fitch KR, Feuk L, Perry GH,Andrews TD, et al. Global variation in copy number in the human genome. Nature 2006;444(7118):444-454. [ Links ]
]]>36. Wong KK, deLeeuw RJ, Dosanjh NS, Kimm LR, Cheng Z, Horsman DE, et al. A comprehensive analysis of common copy-number variations in the human genome.Am J Hum Genet 2007;80(1):91-104. [ Links ]
37. Maino R. Proteómica. El desafío de la post-genómica, Med.Interna, 2007. [ Links ]
38.Teramoto N, Sarker AB,Tonoyama Y,Yoshino T, Hayashi K,Takahashi K, et al. Epstein-Barr virus infection in the neoplastic and nonneoplastic cells of lymphoid malignancies. Cancer 1996;77(11):2339-2347. [ Links ]
39. Colville-Nash PR,Willoughby DA. Growth factors in angiogenesis: current interest and therapeutic potential. Mol Med Today 1997;3(1):14-23. [ Links ]
40.Toi M, Kondo S, Suzuki H,Yamamoto Y, Inada K, Imazawa T, et al. Quantitative analysis of vascular endothelial growth factor in primary breast cancer. Cancer 1996;77(6):1101-1106. [ Links ]
]]>41. Maciag T. Mecanismos moleculares y celulares de la angiogénesis. En: De Vita V, ed.Avances en Oncología. España: Espaxs Publicaciones Médicas, 1990:109-127. [ Links ]
42. Liotta L. Factores de motilidad autocrina tumoral. En: De Vita V, ed. Avances en Oncología. España: Espaxs Publicaciones Médicas, 1988:33-49. [ Links ]
43. Halachmi S, Marden E, Martin G, MacKay H,Abbondanza C, Brown M. Estrogen receptor-associated proteins: possible mediators of hormoneinduced transcription. Science 1994;264(5164):1455-1458. [ Links ]
44. Khan SA, Rogers MA, Obando JA,Tamsen A. Estrogen receptor expression of benign breast epithelium and its association with breast cancer. Cancer Res 1994;54(4):993-997. [ Links ]
45. Liotta L. Invasión de las células cancerosas y metástasis. Investig Cienc 1992;187:24-48. [ Links ]
]]>46. Urterger A. Los componentes de la matriz extracelular como blanco de terapias antimetastásicas. Nuevas Tendencias en Oncología 1997;6 (4):273-279 [ Links ]
47. Sheu J, Shih Ie M. HLA-G and immune evasion in cancer cells. J Formos Med Assoc 2010;109(4):248-257. [ Links ]
48. Old J. El factor de necrosis tumoral. Investig Cienc 142 1988; 20-28. [ Links ]
49. Rosemberg S, et al. Linfocitos infiltrantes del tumor. En: De Vita V, ed. Avances en Oncología. España: Espaxs Publicaciones Médicas, 1990:37-63. [ Links ]
50. Rosemberg S. Inmunoterapia del cáncer. Investig Cienc 1990;166:26-42. [ Links ]
51. Carosella ED, Moreau P, Le Maoult J, Le Discorde M, Dausset J, Rouas-Freiss N. HLA-G molecules: from maternal-fetal tolerance to tissue acceptance.Adv Immunol 2003;81:199-252. [ Links ]
52. Habergger A.Alelos de HLA clase I y II implicados en la susceptibilidad y resistencia a la infección por HIV y en la progresión del SIDA (tesis). Universidad de Buenos Aires Argentina 2005;33-47. [ Links ]
 Autor de correspondencia:
Autor de correspondencia:
Dra. María Teresa Martín de Civetta.
Rivadavia 1150 (3400)
Corrientes, Argentina.
Correo electrónico: mtmcivetta@yahoo.com
Fecha de aceptado: 27 de septiembre de 2011
]]>