Efectos de cruzamiento para producción de leche y características de crecimiento en bovinos de doble propósito en el trópico húmedo*
Effects of crossbreeding on milk production and growth characteristics in dual-purpose cattle in the humid tropics
Sergio Iván Román-Ponceac, Felipe de Jesús Ruiz-Lópezb, Hugo H. Montaldoc, Rita Rizzid, Heriberto Román-Poncee
a Campo Experimental Valles Centrales de Oaxaca. Centro de Investigación Regional Pacifico Sur, INIFAP-SAGARPA, México.
]]> b Centro Nacional de Investigación en Fisiología y Mejoramiento Animal, INIFAP-SAGARPA, México. Km.1 Carr. Ajuchitlan-Colon. 76280. Ajuchitlan, Querétaro, México. Tel. +52 (419) 292-0033. ruiz.felipe@inifap.gob.mx. Correspondencia al segundo autor.c Departamento de Genética y Bioestadística, Facultad de Medicina Veterinaria y Zootecnia, Universidad Nacional Autónoma de México, México D.F.
d Dipartimento di Scienze Veterinarie per la Salute Animale e la Sicurezza Alimentare. Università degli Studi di Milano. Milano, Italy.
e Centro de Investigación Regional Golfo-Centro, INIFAP-SAGARPA, México.
Recibido el 30 de octubre de 2012.
Aceptado el 10 de enero de 2013.
Resumen
Con el objetivo de evaluar los efectos de cruzamiento en tres subpoblaciones de ganado bovino cruzados de doble propósito en el trópico húmedo se utilizaron 5,040 lactancias y pesajes corporales al nacimiento [4,429] y pesos ajustados a 205 [3.878], 365 [3,017] y 540 [2,276] días (PN, P205, P365 y P540, respectivamente) de Cebú (CE) y sus cruzas con Holstein (HS), Suizo Pardo (SP) y Simmental (SM). Los efectos aditivos directos de raza (PG), heterocigocidad (HT) y pérdidas por recombinación (RC) se estimaron mediante un análisis de regresión a través de modelos mixtos. Los efectos fijos fueron el hato y año de parto, época, número de lactancia y sexo de la cría para producción total de leche (PL), así como el hato, y año de nacimiento y época para crecimiento corporal. Los efectos aleatorios para PL fueron el efecto genético directo (animal) y el ambiente permanente. Para crecimiento corporal fueron los efectos genéticos directos y maternos, así como los efectos ambientales permanentes maternos. Se obtuvieron efecto (P<0.10) de PG/HS, PG/SP y HT/SM sobre PL y PG/SP, PG/SM, HT/SM y RC/HS sobre PN. PG/HS y PG/SP presentaron efecto (P<0.10) sobre P205, P365 y P540 y PG/SM sólo sobre P205. Para P205, P365 y P540 hubo efecto (P<0.10) de HT y RC en todas las cruzas. Los resultados aquí presentados permitirán establecer algunas estrategias de aprovechamiento de los efectos genéticos aditivos y no aditivos presentes en las poblaciones cruzadas de bovinos de doble propósito en el trópico húmedo.
]]> Palabras clave: Cruzamiento, Heterocigosidad, Recombinación, Doble propósito.
Abstract
Crossbreeding effects were evaluated in three dual purpose bovine sub-populations in the tropics, and 5,040 lactations, 4,429 birth weights and adjusted weights at 205 [3,878], 365 [3,017] and 540 [2,276] days (PN, P205, P365 y P540, respectively) from Zebu cattle (CE) and its crosses with Holstein (HS), Brown Swiss (SP) and Simmental (SM). Additive direct breed effects (PG), heterozygosity (HT) and recombination loss (RC) were estimated by a regression analysis within breed group with mixed models. Evaluated fixed effects were herd and year of freshening, season, lactation number and offspring gender for milk yield (PL) and herd, birth year and season for growth traits. Random effects for PL were direct (animal) and permanent environment and for growth traits were genetic direct and maternal and permanent maternal environmental effects. PG/HS, PG/SP y HT/SM had effects (P<0.10) on PL while PG/SP, PG/SM, HT/SM and RC/HS on PN. PG/HS y PG/SP presented effects (P<0.10) on P205, P365 and P540 while PG/SM only on P205. HT and RC had effects (P<0.10) on P205, P365 y P540 for all crosses. Results hereby presented will allow the formulation of strategies for the use of additive and non-additive genetic effects of the crossbred populations present in the Mexican humid tropical regions.
Key words: Crossbreeding, Heterozygocity, Recombination Loss, Dual purpose.
INTRODUCCIÓN
El sistema de producción de bovinos de doble propósito (SDP) es el predominante en la región tropical húmeda de México. Cuenta con 2.4 millones de vacas que representan cerca del 60 % de las que se dedican a la producción de leche en esta región. Este sistema de producción aporta a nivel nacional alrededor del 19.5 % de la leche y el 40 % de la carne(1,2). En este sistema la producción diaria de leche promedio por vaca es de 3 a 9 kg, en una lactación que dura alrededor de 120 a 180 días y con un parto cada 18 a 24 meses(1,2).
La mayor parte de los animales en el SDP, son producto de distintos cruzamientos de razas europeas (Bos taurus taurus, Linnaeus, 1758) con razas cebuinas (Bos taurus indicus, Linnaeus, 1758), o con ganado local de origen desconocido, comúnmente llamado criollo(2). Las bases teóricas de los sistemas de cruzamiento han sido discutidas anteriormente por diversos autores, donde han utilizado efectos genéticos aditivos y no aditivos en la modelación de las medias de las cruzas(3,4,5). Los efectos de cruzamiento son los efectos aditivos directos de raza, heterosis y recombinación o epistasis(4,5).
Se ha propuesto el uso de modelos de regresión múltiple para la estimación de los efectos de cruzamiento. Para esto se incluye la fracción esperada de genes de una raza (PG), donde se logra estimar el efecto aditivo directo de raza y los coeficientes de heterocigosidad (HT)(4,5,6) y de recombinación (RC)(7,8,9) por medio de los cuales se busca estimar la heterosis y recombinación o epistasis, respectivamente.
]]> La estimación de los efectos de cruzamiento en poblaciones específicas permite predecir el comportamiento productivo esperado de diferentes cruzas, así como establecer esquemas de evaluación genética con la finalidad de seleccionar a los reproductores a través de su valor genético aditivo, sin los sesgos ocasionados por los efectos de heterosis y recombinación en poblaciones multiraciales(3,9).El objetivo de este trabajo fue estimar los efectos genéticos directos de raza, heterosis y de pérdidas por recombinación en poblaciones multirraciales de bovinos de doble propósito en el trópico húmedo de México, para la producción total de leche y características de crecimiento.
MATERIALES Y MÉTODOS
Datos productivos
Se utilizaron los registros productivos y genealógicos de seis hatos del Instituto Nacional de Investigaciones Forestales, Agrícolas y Pecuarias (INIFAP) en cinco Campos Experimentales (CEx): dos hatos en el CEx La Posta y un hato en el CEx de Playa Vicente, ambos en el Estado de Veracruz, CEx Las Margaritas en la Sierra Oriente del estado de Puebla, CEx Matías Romero en Oaxaca y CEx Balancán en Tabasco.
Para la realización de este estudio se utilizaron 5,040 lactancias de cruzas de Cebú (CE) con Holstein (HS) [2,253], Suizo Pardo (SP) [1,921] y Simmental (SM) [866].
Producción total de leche. La producción de leche se registró diariamente al momento de la ordeña, calculando la producción total por lactación (PL) con la suma de las producciones diarias durante todo el periodo. Sólo se incluyeron lactaciones con un mínimo de 90 días y hasta un máximo de 800 días.
Características de crecimiento. Se analizaron los siguientes pesos corporales: peso al nacimiento [4,398] y pesos ajustados a los 205 [3,878], 365 [3,017] y 540 [2,276] días de edad (PN, P205, P365 y P540, respectivamente) de acuerdo con la metodología descrita por BIF (Beef Improvement Federation)(10).
Alimentación.
]]> Los animales se alimentaron con base en gramíneas tropicales y suplementados con mezclas de sales minerales ad libitum. Los periodos de ocupación de los potreros variaron entre uno a tres días, y los periodos de descanso fueron aproximadamente de 35 a 40 días, dependiendo de la época del año y de la especie forrajera. Durante la época de sequía se complementó la alimentación del ganado con forrajes de corte en fresco o conservados. Las vacas recibieron un alimento concentrado comercial (16 % de proteína cruda y 70 % de total de nutrimentos digestibles) al momento de la ordeña por la mañana y por la tarde. El sistema de crianza de los becerros fue amamantamiento restringido, salvo en un hato del CEx La Posta, donde se utilizó crianza artificial con destete a los 90 días.Estructura y origen de las subpoblaciones
La estructura poblacional en los hatos estuvo integrada por tres subpoblaciones de cruzas de razas especializadas (HS, SP y SM). Estas subpoblaciones no tuvieron apareamientos entre ellas, pero sí compartieron el manejo y alimentación dentro del hato. Una parte de las subpoblaciones HS y SP tuvieron su origen en vacas puras importadas de Canadá y Estados Unidos. Estas vacas se sirvieron con semen de toros Cebú de importación, principalmente Brahman. La otra parte de la población tiene su origen en hembras Cebú, principalmente Indubrasil y Brahman, que se sirvieron con semen de toros importados de las razas HS, SP y SM.
Al inicio, el sistema de cruzamiento utilizado fue rotacional de dos razas, donde se alternaban dos generaciones de toros de razas especializadas y una generación de raza cebuina. Posteriormente, el esquema de cruzamiento fue modificado a la utilización de sementales cruzados con la finalidad de mantener las poblaciones en un rango de proporción de raza especializada que variaba entre 50 y 75 %.
Análisis estadístico
Todos los análisis se realizaron mediante la metodología de modelos mixtos utilizando el programa ASReml(11).
Efectos de cruzamiento: El efecto directo de Raza (PG) se expresó como el porcentaje de la raza europea con respecto al Cebú.
El coeficiente de heterocigocidad (HT) y el coeficiente de pérdidas por recombinación (RC) se estimaron de la siguiente manera:
HT=(Ps*(1-Pm))+(Pm*(1-Ps))(4,5,6)
RC=((Ps*(1-Ps))+(Pm*(1-Pm)))(7,8,9)
]]> Donde: PS= PG del padre. PM= PG de la madre.Producción total de leche. Para la estimación de los efectos de cruzamiento se utilizó un modelo de repetibilidad que incluyó PG, HT y RC. Los efectos ambientales considerados en el modelo como efectos fijos fueron el hato y año de parto, época (lluvias y secas), numero de lactancia (1 a 3 o más) y sexo de la cría. La ecuación del modelo fue la siguiente:
y= Xp + Qn + Z1u + Z2pe + e
Donde: y= vector de los registros de producción total de leche; X= matriz de incidencia para los efectos fijos (hato, año, época y sexo de la cría); Q= matriz de incidencia para los coeficientes de regresión de PG, HT y RC; Z1= matriz de incidencia para los efectos genéticos directos del animal; Z2 = matriz de incidencia para el efecto aleatorio del ambiente permanente; 3= vector de efectos fijos; n = vector de coeficientes de regresión de PG, HT y RC; u= vector de efectos genéticos directos del animal (u ~ N(0, Aó2u); pe= vector de efectos aleatorios del ambiente permanente (pe ~ N(0, Iσ2pe); e= vector de residuos (e ~ N(0, Iσ2e).
Crecimiento corporal. Se utilizaron registros de pesos corporales al nacimiento y pesos ajustados a los 205, 365 y 540 días de edad (PN, P205, P365 y P540, respectivamente) de CE y cruzas de CE con HS, SP y SM. Para la estimación de los efectos de cruzamiento se incluyeron las covariables de PG, HT y RC utilizando un modelo animal que incluyó los efectos genéticos, directos, maternos y ambientales permanentes(12-15). Los efectos ambientales considerados en el modelo como efectos fijos fueron el hato, año y época de nacimiento (lluvias y secas). La época de lluvia fue definida desde los meses de junio hasta noviembre; la época de secas el resto de los meses del año.
La ecuación del modelo utilizado para el análisis de PN, P205 y P365 fue:
y= Xp + Qn + Z1u + Z3m + Z4pe + e
Donde: X, Q, Z1, β, n, u, y e ya fueron definidos en el modelo anterior; y= vector de las observaciones (PN, P205 y P365); Z3= matriz de incidencia para los efectos genéticos aditivos maternos; Z4= matriz de incidencia para los efectos ambientales permanentes maternos; m= vector de efectos genéticos aditivos maternos (m ~ N(0, Aσ2m); pe= vector de efectos aleatorios maternos ambientales permanentes (pe ~ N(0, Iσ2pe).
La covarianza entre el vector de los efectos directos (u) y el vector de los efectos maternos (m) fue igual a Aσum, donde A= matriz de relaciones aditivas, y σum = covarianza entre efectos genéticos directos y maternos. En análisis preliminares previos para P205 y P365 la prueba de razón de verosimilitudes no mostró efecto de la inclusión de la covarianza sobre los estimados, por lo cual se decidió fijar como cero (= 0).
Finalmente para el peso a los 540 días se utilizó el modelo y= Xβ + Qn + Z1u + e; donde los términos del modelo son los mismos que los incluidos en los modelos anteriores.
]]>RESULTADOS
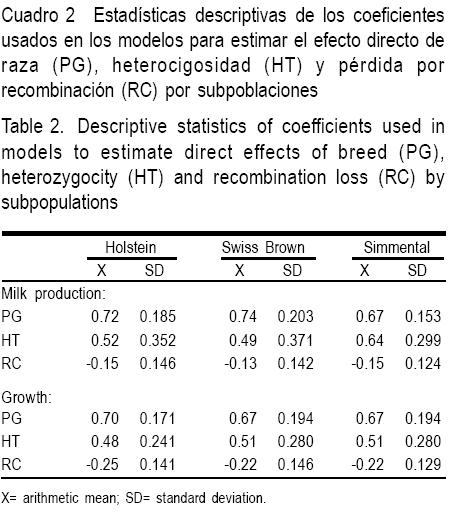
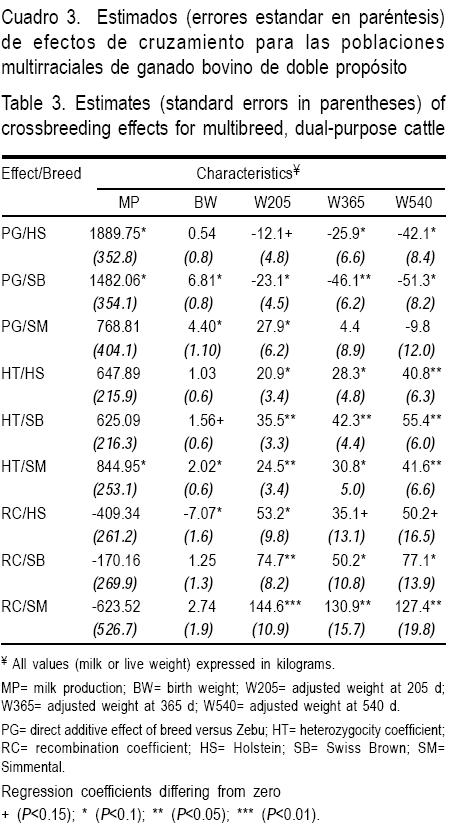
Las estadísticas descriptivas para la producción de leche y pesos corporales en la subpoblación de cruzas de HS, SP y SM se presentan en el Cuadro 1. En el Cuadro 2 se muestran las estadísticas de los efectos de cruzamiento (PG, HT y RC) para cada una de las subpoblaciones y para las características de producción de leche y crecimiento corporal (Cuadro 2). En el Cuadro 3 se observan los estimados de PG, HT y RC.

Efecto directo de raza
Los efectos fijos aditivos de raza (PG) sobre PL en las cruzas de HS y SP fueron significativos (P<0.10). Para el caso de PN y P205 los PG fueron significativos en las subpoblaciones SP y SM (P<0.10). En cambio, para P540, fueron significativos en las subpoblaciones cruzadas de HS y SP (P<0.10), como se muestra en el Cuadro 3.
Heterosis
]]> Sólo la subpoblación SM presentó valores de HT significativos (P<0.10) para PL y PN. Todas las subpoblaciones presentaron valores de HT estadísticamente significativos para los pesos P205, P365 y P540 (Cuadro 3).Pérdidas por recombinación
No se encontraron pérdidas por recombinación significativas para PL (P>0.10). En el caso de las características de crecimiento, RC sólo fue importante (P<0.10) para PN de la subpoblación de cruzas HS y para P205, P365 y P540 en las subpoblaciones cruzadas SP y SM (Cuadro 3).
DISCUSIÓN
Los resultados sugieren la necesidad de incluir los efectos de cruzamiento durante la predicción de valores genéticos, ya que representan una fuente de variación importante en las poblaciones multirraciales y características aquí estudiadas.
La producción de leche de las cruzas de HS fue superior en un 21.6 % con respecto a las cuzas con SP, lo cual es consistente con lo encontrado en otras poblaciones de ganado bovino cruzado en condiciones tropicales(16); pero inferior a lo observado en poblaciones multirraciales en África(12). Los efectos genéticos aditivos de raza han sido estimados tanto en poblaciones cruzadas como entre poblaciones de ganado lechero, tal es el estudio entre la población de Holstein de Reino Unido y Estados Unidos de América, donde se estimó un PG positivo para el efecto aditivo de la población americana sobre la inglesa(4,5).
Los efectos genéticos aditivos directos positivos de la raza HS para peso al destete han sido previamente informados en algunas poblaciones cruzadas de doble propósito en África(12). De igual manera, se han estimado efectos positivos de PG de razas especializados en la producción de carne en las razas B. taurus; aunque la magnitud de los estimados varía dependiendo de la separación filogenética o especialización de las poblaciones de las razas. Un factor adicional a tomar en cuenta son las condiciones ambientales, sistemas de producción y los objetivos de selección presentes en las poblaciones parentales, ya que no necesariamente corresponden a las condiciones de las poblaciones cruzadas(17). Por lo que esta situación se sugiere como posible causa de los estimadores negativos de PG en las características de crecimiento (P205, P365 y P540).
Los estimados de heterosis obtenidos en el presente trabajo siempre fueron significativos para la cruza de SM con CE (P<0.10) en todas las características, en cambio para las cruzas de CE con HS y SP sólo tuvieron efecto significativo para P205, P365 y P540. El resto de los estimadores tienden a ser positivos, pero no difieren de cero. La heterosis estimada para PL en poblaciones cruzadas de B. taurus taurus x B taurus indicus ha sido informada con valores aproximados de 18 % en poblaciones resultado de la cruza de HS, SP y Jersey con CE(17). Otros estudios donde se incluyeron poblaciones cruzadas B. taurus taurus x B. taurus taurus y B. taurus taurus X B. taurus indicus confirman lo anterior con las cruzas de SP con CE(12). Estudios similares en poblaciones de raza Holstein han demostrado la presencia de efectos positivos de heterosis en cruzamientos entre poblaciones de distintos países como por ejemplo entre Estados Unidos de América y el Reino Unido, en cuyo caso, los autores lo atribuyen a la divergencia entre ambas poblaciones debida a procesos de selección diferentes(4,5).
En poblaciones cruzadas especializadas en la producción de carne tanto B. taurus taurus como B. taurus taurus X B. taurus indicus se ha estudiado la heterosis para crecimiento corporal, características de la canal y eficiencia productiva. La información disponible en poblaciones cruzadas de doble propósito es limitada, debido al énfasis económico que se ha tenido en la producción de leche en los programas de cruzamiento en este sistema productivo tropical. Los resultados presentados en poblaciones cruzadas B. taurus taurus X B. taurus indicus en condiciones tropicales de África informan de efectos significativos de heterosis sobre el peso al destete y al año (P<0.10)(7,8). Por lo que el mantenimiento de heterosis adecuados podrá representar ventajas económicas con base a un mejor comportamiento productivo.
]]> La ruptura de efectos de interacciones interlocus (epistasis) en el genoma permiten explicar algunas desviaciones en el comportamiento productivo en poblaciones cruzadas B. taurus taurus X B. taurus indicus. Los resultados demuestran un decremento en la producción de leche en base a los estimados de recombinación(17). Sin embargo, otros resultados muestran un efecto positivo de la recombinación en la producción de leche en una población cruzada de Ayrshire con Cebú en el trópico africano(17). Cabe hacer mención que los estimadores presentados en este estudio para recombinación no fueron significativamente diferentes de cero (P>0.10), lo que nos sugiere que el sentido y magnitud de los estimadores de recombinación varían de acuerdo a las razas involucradas en el cruzamiento.De la misma manera, los estimados de recombinación presentados para las características de crecimiento en poblaciones cruzadas B. taurus taurus X B. taurus indicus en condiciones tropicales son escasos y no son siempre consistentes entre ellos. Los estimadores de recombinación obtenidos en poblaciones cruzadas y en condiciones tropicales se han presentado con signo negativo para peso al destete y al año de edad, aunque no para todas las cruzas incluidas (P<0.10)(7,8).
CONCLUSIONES E IMPLICACIONES
Las poblaciones cruzadas de bovinos de doble propósito en el trópico mexicano requieren del desarrollo de procesos de evaluación genética que permitan predecir los valores genéticos aditivos de los animales de modo no sesgado y preciso. Los resultados presentados demuestran la importancia que tiene la inclusión de los efectos aditivos directos de raza, heterosis y recombinación, en los modelos de evaluación genética para el desarrollo de programas de cruzamiento y selección en poblaciones multirraciales. Las estimaciones de los efectos de cruzamiento dependen tanto de las razas involucradas como del medio ambiente y el sistema de producción en el cual se van a utilizar. Finalmente se concluye que pese a no ser estadísticamente significativo en todos los casos, la omisión de los efectos de cruzamiento en los programas de mejoramiento genético en este tipo de poblaciones generaría sesgos en la predicción de valores, y por ende en la estimación y evaluación del comportamiento productivo de los animales en este sistema de producción.
AGRADECIMIENTOS
Los autores agradecen a la Compañía "Nestlé México" SA de CV por el financiamiento del Proyecto de Mejoramiento Genético de Ganado Bovino de Doble Propósito en el Trópico Mexicano del INIFAP, al Consejo Nacional de Ciencia y Tecnología (CONACYT) por la beca otorgada al primer autor durante el desarrollo del programa de maestría y al Programa Ejecutivo de Cooperación Científica y Tecnológica México - Italia 2007-2009 a través del Proyecto "Evaluación del Genotipo de Bovinos Cruzados Utilizados en Sistemas de Doble Propósito en Climas Tropicales". Los resultados del presente trabajo no reflejan la opinión o punto de vista de la compañía Nestlé México, CONACYT o el Programa Ejecutivo de Cooperación Científica y Tecnológica México - Italia.
LITERATURA CITADA
]]>1. Dios Vallejo OO. Ecofisiología de los bovinos en sistemas de producción del trópico húmedo. Primera ed. México. Universidad Juárez Autónoma de Tabasco. 2001. [ Links ]
2. Koppel RET, Ortiz OGA, Ávila DA, Lagunes LJ, Castañeda MOG, López GI, Aguilar BU, et al. Manejo de ganado bovino de doble propósito en el trópico. INIFAP-CIRGOC. Libro técnico Num. 5. 2a ed. Veracruz. México.2002. [ Links ]
3. Van Der Werf JHJ, De Boer W. Estimation of genetic parameters in a crossbred population of black and white cattle. J Dairy Sci 1989;72(10):2615-2623. [ Links ]
4. Akbas Y, Brotherstone S, Hill WG. Animal model estimation of non-additive genetic parameters in dairy cattle, and their effect on heritability estimation and breeding value prediction. J Anim Breed Genet 1993;110(1-6):105-113. [ Links ]
5. Brotherstone S, Hill WG. Estimation of non-additive genetic parameters for lactations 1 a 5 and survival in Holstein-Friesian dairy cattle. Livest Prod Sci 1994;40(2):115-122. [ Links ]
]]>6. Arthur PF, Hernsshaw H, Stephenson PD. Direct and maternal additive and heterosis effects from crossing Bos indicus and Bos taurus cattle: cow and calf performance in two environments. Livest Prod Sci 1999;57(3):231-241. [ Links ]
7. Demeke S, Neser FWC, Schoeman SJ. Early growth performance of Bos taurus X Bos indicus cattle crosses in Ethiopia: Evaluation of different crossbreeding models. J Anim Breed Genet 2003;120(1):39-50. [ Links ]
8. Demeke S, Neser FWC, Schoeman S. Early growth performance of Bos taurus X Bos indicus cattle crosses in Ethiopia: Estimation of individual crossbreeding effects. J Anim Breed Genet 2003;120(4):245-257. [ Links ]
9. Hirooka H, Groen AbF, Van der Werf, JHJ. Estimation of additive and non-additive genetic parameters for carcass traits on bulls in dairy, dual purpose and beef cattle breed. Livest Prod Sci 1998;54(2):99-105. [ Links ]
10. BIF. Beef Improvement Federation. Guidelines for uniform beef improvement programs. 8th ed. The University of Georgia, Athens. 2002. [ Links ]
]]>11. Gilmour AR, Gogel BJ, Cullis BR, Welham SJ, Thompson R. ASReml User Guide (Release 1.0). VSN International Ltd, Hemel Hempstead, UK. 2002. [ Links ]
12. Kahi AK, Thorpe W, Nitter G, Baker RL. Crossbreeding for dairy production in the lowland tropics of Kenya. I. Estimation of individual crossbreeding effects on milk production and reproductive traits and on cow live weight. Livest Prod Sci 2000;63(1):39-54. [ Links ]
13. Meyer K, Carric MJ, Donnelly BJP. Genetic parameters for milk productions of Australian beef cows and weaning weight of their calves. J Anim Sci 1994;(72):1155-1165. [ Links ]
14. Groeneveld E, Mostert BE, Rust T. The covariance structure of growth traits in the Afrikaner beef population. Livest Prod Sci 1998;55(2):99-107. [ Links ]
15. Tosh JJ, Kemp RA, Ward DR. Estimates of direct and maternal genetic parameters for weights and backfat thickness in a multibreed population of beef cattle. Can J Anim Sci 1999;79(4):433-439. [ Links ]
]]>16. Syrstad O.Relative Mertis of vatious Bos taurus dairy breeds for cross-breeding with Bos indicus cattle. Livest Prod Sci 1985;13(4):351-357. [ Links ]
17. Syrstad O. Heterosis in Bos taurus X Bos indicus crosses. Livest Prod Sci 1985;12(4):299-307. [ Links ]
18. Miller SP, Wilton JW. Genetic relationship among direct and maternal components of milk yield and maternal weaning gain in a multibreed beef herd. J Anim Sci 1999;77(5):1155-1161. [ Links ]
* Este trabajo es parte de la Tesis de Maestría del primer autor. Proyecto financiado por: Proyecto de Mejoramiento Genético del Ganado Bovino de Doble Propósito en el Trópico INIFAP-NESTLE. Convenio de Cooperación Científica y Tecnológica México - Italia 2003 - 2005. SRE.
]]>