MLPA (amplificación de sondas dependiente de ligandos
múltiples) en el diagnóstico perinatal rápido de las principales aneuploidías
MLPA (multiplex ligation-dependent probe amplification) in perinatal rapid diagnosis of major aneuploidies
Higinio Estrada-Juárez,* Liliana Fernández-Hernández,‡ Carlos Rivera-Pedroza,‡ Patricia Grether-González *
* Departamento de Genética. ]]> ‡ Estudiante del Curso de Alta Especialidad en Genética Perinatal
Instituto Nacional de Perinatología ''Isidro Espinosa de los Reyes''.
Trabajo apoyado parcialmente por el proyecto FONCICYT, núm. 95419.a
Correspondencia:
Dra. Patricia Grether González
Montes Urales Núm. 800,
Col. Lomas Virreyes,
11000, México, D.F. ]]>
Correo electrónico: pgrether@gmail.com
Recibido: 07 de mayo de 2012
Aceptado: 19 de julio de 2012
RESUMEN
Introducción: El MLPA (amplificación de sondas dependiente de ligandos múltiples) es un método reciente, basado en la reacción en cadena de la polimerasa (RCP), de cuantificación relativa del número de copias normales y anormales de ácido desoxirribonucleico (ADN) de hasta 40 secuencias genómicas diferentes. Su uso se ha difundido tanto en la investigación como en el diagnóstico clínico. Recientemente, el MLPA se ha utilizado en diagnóstico prenatal y en el estudio de abortos. Objetivo: Presentar los primeros resultados obtenidos con MLPA en el diagnóstico perinatal de las principales aneuploidías de los cromosomas 13, 18, 21, X y Y. Material y métodos: Se obtuvo ácido desoxirribonucleico genómico de tejidos sin cultivar de aborto, biopsia de vellosidades coriales (VC), líquido amniótico (LA), cordón umbilical (CU) de óbitos o sangre periférica (SP) de recién nacidos, en 13 casos con patología perinatal. Para el MLPA se utilizó el kit p 290 para diagnóstico prenatal y sus productos se cuantificaron en un secuenciador ABI Prism 3130. Todos los casos se procesaron para cariotipo en forma paralela. Resultados: Se obtuvieron resultados con MLPA entre dos y tres días en las 13 muestras estudiadas. Seis de ellas mostraron aneuploidías. El cariotipo se obtuvo entre 15 y 21 días en 11 casos, cinco fueron aneuploides y dos fallaron. Los resultados entre MLPA y cariotipo fueron concordantes en las fallas del cultivo celular, el diagnóstico se obtuvo por MLPA. Conclusiones: El MLPA es un método útil y rápido en el diagnóstico perinatal de las principales aneuploidías; además, tiene la ventaja de permitir estudiar tejidos con baja viabilidad celular como ocurre en algunos casos de aborto u óbito.
Palabras clave: Diagnóstico prenatal, aneuploidía, cariotipo, MLPA.
ABSTRACT
]]> Introduction: The MLPA (multiplex ligation-dependent probe amplification) is a new method based on polimerase chain reaction (PCR) for relative quantification of normal and abnormal numbers of copies of desoxyribonucleic (DNA), up to 40 different genomic sequences. Its use is widespread in both, research and clinical diagnosis. MLPA recently began to be used in prenatal diagnosis and study of pregnancy losses. Objective: Present the first results obtained with MLPA in perinatal diagnosis of major aneuploidies of chromosomes 13, 18, 21, X and Y. Methods: Genomic DNA was obtained from different uncultivated tissues: abortion, chorionic villus, amniotic fluid, umbilical cord blood or peripheral blood in 13 cases with perinatal pathology. MLPA kit p290 for prenatal diagnosis was used and its products were quantified in ABI Prism 3130 sequencer. All cases were processed in parallel for karyotype. Results: MLPA results were obtained in 2 to 3 days in the 13 samples studied. Six of them showed aneuploidy. Karyotype was obtained between 15 and 21 days in 11 cases, five were aneuploidy and two failed. The results obtained with MLPA and karyotypes were concordant and in cases where the cell culture failed, the diagnosis was obtained by MLPA. Conclusions: MLPA is a rapid and useful method in the perinatal diagnosis of major aneuploidies, it also has the advantage of allowing the study of tissues with low cell viability, as in some cases of abortion and fetal death.Key words: Prenatal diagnosis, aneuploidy, karyotype, MLPA.
Introducción
Las anomalías cromosómicas son una causa bien establecida de pérdida de la gestación. Las más comunes son aneuploidías autosómicas (~ 75%), seguidas de poliploidía (~ 13%), anomalías de los cromosomas sexuales (~ 8%) y rearreglos estructurales no balanceados (~ 4%).1,2 Las trisomías de los cromosomas 21, 13 o 18, así como las aneuploidías de los sexocromosomas, engloban aproximadamente el 95% de cariotipos fetales anormales detectados en cultivos de células de líquido amniótico (LA).3 Durante más de cinco décadas, las anormalidades cromosómicas en la etapa prenatal se han identificado mediante citogenética convencional, que requiere de células cultivadas. Su resultado depende del número de células en división, por lo que el diagnóstico generalmente está disponible en 10 a 15 días.4,5 En el cariotipo, la resolución es de aproximadamente 5 a 10 Mb, lo que hace pérdidas o ganancias menores que fácilmente pasan desapercibidas como ocurre en la mayoría de los síndromes por microdeleción o microduplicación.
En los últimos años, las técnicas moleculares se han vuelto más asequibles, permitiendo el diagnóstico en tiempos tan cortos como 48 a 72 horas y utilizando células no cultivadas. Las principales técnicas son el FISH (Fluorescence in situ hybridization) y la QF-PCR (Quantitative fluorescence polimerase chain reaction) . En el FISH se utilizan sondas marcadas con fluorocromos de diferentes colores con las que se detecta el número de centrómeros de los cromosomas de interés, permitiendo observar variaciones en el número de cromosomas específicos. El FISH es un método laborioso con limitaciones en su aplicación a nivel diagnóstico, particularmente en centros con grandes volúmenes de muestras. La QF-PCR se basa en la amplificación y detección semicuantitativa de algunos segmentos de ácido desoxirribonucleico (ADN: DNA, desoxyribonucleic acid) de cromosomas específicos, por medio de la unión de cebadores únicos para cada región. Al amplificarse los marcadores polimórficos para los cromosomas de interés (13, 18, 21, X y Y) se obtiene una gráfica con picos que indican el número de alelos de las regiones investigadas.
La UK Health menciona que QF-PCR es tan fiable y precisa como FISH y cariotipo para las aneuploidías definidas, con una sensibilidad y especificidad del 95.65 y 99.97%, respectivamente. Además, se detecta de forma fiable la triploidía. Una ventaja importante sobre el FISH es la posibilidad de la automatización y el procesamiento por lotes de muestra, lo que disminuye el costo individual.6
Recientemente se ha difundido otra metodología que es el ensayo de MLPA, desarrollado por la empresa MRC-Holland y publicado en 2002 como un método semicuantitativo para el análisis selectivo de los cambios en el número de copias del ácido desoxirribonucleico.7 Se ha desarrollado un ensayo comercial de MLPA basado en la discriminación de longitud de los productos de ligación para la detección de aneuploidías en los cromosomas X, Y, 13, 18 y 21. Este ensayo puede incluir también 20 síndromes por microdeleción con implicaciones clínicas.
Estudios previos han demostrado que MLPA es una prueba apropiada para la aplicación de rutina en el diagnóstico prenatal.3,8-12 Kooper y colaboradores, en 2008, realizaron un estudio en 1,000 LA, concluyendo que es posible utilizar MLPA como prueba única de diagnóstico para las aneuploidías más comunes.11
MLPA permite la cuantificación relativa de hasta 50 secuencias diana diferentes en una reacción y no requiere células vivas o en cultivo celular. Es menos intensiva en trabajo y menos costosa en comparación con cariotipo FISH e incluso QF-PCR. El método de MLPA se ha aplicado ampliamente, además de las aneuploidías, en el diagnóstico molecular de enfermedades genéticas tales como el tipo de distrofia muscular de Duchenne (DMD) y ataxia espinocerebelosa.13,14
]]> Hasta donde sabemos, no hay otros estudios publicados en México que validen el método de MLPA en el diagnóstico prenatal o perinatal de las principales aneuploidías.Objetivo
Los objetivos de este trabajo son presentar los primeros resultados obtenidos en el diagnóstico perinatal de las principales aneuploidías de los cromosomas 13, 18, 21, X y Y utilizando la técnica de MLPA en el laboratorio de genética del Instituto Nacional de Perinatología (INPer) y discutir las ventajas y desventajas de este método con los resultados obtenidos con el estándar de oro que es el cariotipo.
Material y métodos
Durante el periodo de marzo a octubre de 2012, se estudiaron 13 muestras de material de aborto, LA, líquido de higroma cervical fetal, cordón umbilical y sangre periférica de fetos o recién nacidos con anomalías diversas.
El ácido desoxirribonucleico de células de LA y líquido del higroma se aisló mediante la utilización del kit QIAamp DNA mini (Qiagen, Hilden, Alemania); el ADN de células de cordón umbilical, sangre periférica y vellosidades coriales, se aisló por medio del kit Wizard Genomic DNA purification (Promega, Wisconsin, EUA). En ambos casos se sustituyó el buffer de rehidratación del kit por Buffer Tris 0.5mM, y el volumen de solvente sugerido (200 uL) se redujo a 50 uL. Se determinaron los cocientes de absorbancia 260/280 y 260/230.
La prueba de MLPA se efectuó con el kit p290 Lote B1-1009, siguiendo el procedimiento indicado por el fabricante (www.mrc-holland.com). Los productos obtenidos de la reacción en cadena de la polimerasa se cuantificaron por electroforesis capilar en un analizador ABI 3130, modificando tiempo de inyección, tiempo de corrida y voltaje de corrida; el análisis se realizó con el software Coffalyser V 1.0 aplicación propia de MRC-Holland.
Análisis estadístico
Se compararon los electroferogramas, en donde se representa la comparación de las intensidades de fluorescencia (altura) versus el tamaño de la sonda (tamaño en pares de bases), de las muestras con respecto al patrón del kit. Se consideró satisfactoria la prueba cuando las sondas control (Q, D, y tres fragmentos de tamaño constante en 88, 92 y 96 nt) cumplieron los criterios marcados por el fabricante y la altura del pico más bajo fue mayor a un tercio con respecto a la altura del pico más alto.
Se realizó una normalización intramuestra en cada área del pico de la sonda, seguida de una normalización interanalítica con respecto a las dos muestras de referencia normales (un hombre y una mujer) que se corrieron paralelas en el mismo ensayo. Esta normalización es esencial ya que las variaciones en las condiciones experimentales pueden dar lugar a diferencias cuantitativas. Los resultados MLPA se expresan como la relación media por cromosoma con un intervalo de confianza (IC) del 95%. Al hacerlo, el valor medio esperado de 1.0 representa dos copias de la secuencia diana en la muestra, mientras que una o tres copias de la secuencia diana en número espera valores medios de 0.75 o 1.25, respectivamente.
]]> ResultadosSe muestran los primeros resultados de MLPA en el INPer que comprenden el diagnóstico de 13 muestras perinatales. Once casos fueron fetos o recién nacidos que tuvieron datos ultrasonográficos o clínicos de enfermedad fetal, un recién nacido aparentemente sano y un caso de aborto espontáneo de primer trimestre. De los siete casos de diagnóstico prenatal, en seis se estudió LA y en uno el líquido de higroma cervical fetal. Hubo dos óbitos y un aborto espontáneo en los que se estudió cordón umbilical en los dos primeros y vellosidades coriales en el último. Finalmente, en tres casos el estudio se realizó en sangre periférica de recién nacidos vivos.
El ácido desoxirribonucleico genómico se extrajo de las células sin cultivar de cinco distintos tipos de tejido. Las cantidades y calidad obtenidas se muestran en el cuadro I.
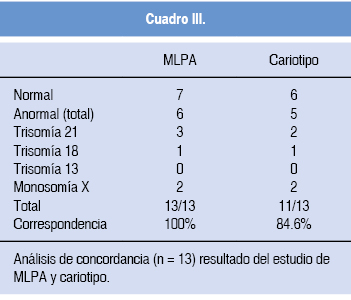
En los 13 casos fue posible obtener el diagnóstico por MLPA, y al compararlos con los resultados obtenidos por cariotipo se observó concordancia en los 11 casos con ambos resultados. En dos casos (cordón umbilical en óbitos) el cultivo celular falló, por lo que el cariotipo no se pudo obtener; sin embargo, el MLPA sí permitió tener un resultado. En el cuadro II se muestra el resultado del MLPA y el cariotipo, así como el diagnóstico clínico a la resolución de la gestación. Las dos muestras que no se analizaron por cariotipo (CU-1 y CU-2), se interpretaron en MLPA como ''mlpa X:Y(P290)x1; 13,18(P290)x2; 21(P290)x3'', explicándose como masculino compatible con trisomía 21 y la otra como ''mlpa X(P290)x2; 13,18,21(P290)x2'', explicándose como femenino con disomía 13, 18 y 21 (normal). La figura 1 muestra las gráficas de dispersión representativas de los análisis de MLPA. Los resultados del análisis de concordancia de ambas técnicas se muestran en el cuadro III. El tiempo en que se obtuvieron los resultados por medio de MLPA fue de 2.5 días, independientemente del tejido estudiado en comparación con por lo menos 10 días para el cariotipo; los requerimientos para la realización de ambas pruebas se muestran en el cuadro IV.

]]> Discusión
Actualmente se utilizan diferentes métodos basados en la detección de las aneuploidías más comunes en tejidos sin cultivar, como el FISH o QF-PCR, para proporcionar un resultado rápido dentro de 24-48 horas posteriores a la toma de la muestra. En los últimos años, el uso de MLPA para la detección rápida de aneuploidías de los cromosomas X, Y, 13, 18 y 21 ha surgido como una alternativa. Slater y colaboradores evaluaron los resultados del análisis de MLPA para la detección prenatal de las aneuploidías más comunes en un ensayo ciego, prospectivo, realizado en 492 muestras de LA.13 Los resultados muestran que ninguna prueba analizada por MLPA falló y la identificación fue clara en los casos con aneuploidías autosómicas. La determinación del sexo fue también del 100% de precisión. Basándose en estos resultados, los autores sugirieron que MLPA es una prueba rápida, flexible, sensible y robusta para la detección de aneuploidías prenatales. Gerdes y cols. informaron de un estudio sobre 1,593 muestras (809 de LA y 784 de vellosidades coriales) en las que se realizó el diagnóstico prenatal mediante el uso de ambas técnicas, citogenética convencional y MLPA.15 Para los propósitos del estudio, el análisis MLPA se organizó para la finalización y respuesta dentro de dos días desde la recepción de la muestra. Los datos revelaron que MLPA es una técnica confiable, rápida y robusta para proporcionar el resultado rápido. Van Opstal y colaboradores reportaron un estudio prospectivo sobre 4,000 muestras de LA utilizando MLPA para detectar aneuploidías de los cromosomas 13, 18, 21 y sexuales, obteniendo 3,932 concluyentes (98.3%) y 68 (1.7%) resultados no concluyentes.12 Entre los resultados concluyentes, en 76 casos (1.9%) con análisis normal de MLPA, el cariotipo mostró otras anomalías que consistieron en alteraciones estructurales, triploidía 69,XXX, mosaicismo de sexocromosomas, aneuploidías de cromosomas distintos a los investigados y mosaico con un marcador extra. Este es un hallazgo esperado por el diseño propio de la prueba de MLPA para las principales aneuploidías que se presenta también con FISH o QF-PCR. Los resultados no concluyentes de este estudio se debieron a la presencia de contaminación con sangre de la muestra de LA, a cantidad insuficiente de ADN o a razones desconocidas.
En nuestro estudio, aun cuando son pocas muestras, la detección por MLPA ha sido buena. Comparamos el tiempo de entrega de resultados de ambas técnicas y para cariotipo fueron necesarios al menos 10 días; en cambio, por medio de MLPA obtuvimos el reporte con la interpretación en 2.5 días. Por medio de MLPA fue posible conocer el diagnóstico de dos casos en los que el cultivo falló, probablemente debido a que se trataba de tejido obtenido dos o tres días después de la muerte fetal.
Los 11 casos con resultados por ambas técnicas fueron concordantes y en los dos casos con resultado exclusivamente por MLPA, el cuadro clínico fue compatible. Esta metodología introduce una valiosa herramienta en los casos en los que el cultivo celular se compromete por la baja viabilidad de las células, como ocurre en aborto o muerte fetal, y abre la posibilidad diagnóstica en muchos casos de falla por los métodos tradicionales.
Otra ventaja de la técnica de MLPA es que los kits se han complementado con diversas sondas para poder diagnosticar otras patologías como son los síndromes por microdeleción/microduplicación o bien detectar las regiones subteloméricas de todos los cromosomas, lo que nos daría una visión más amplia que abarca al resto de los cromosomas. Hoy en día, el cariotipo sigue siendo el estándar de oro en la detección de las anomalías cromosómicas numéricas y estructurales y en la detección de mosaicismo que con frecuencia no es detectado con las técnicas moleculares; sin embargo, el MLPA representa una alternativa útil, eficiente y precisa en el diagnóstico de la patología genética que se presenta en el periodo perinatal.
Guo y colaboradores desarrollaron un método combinado de MLPA/rtPCR en donde el par de cebadores utilizados para la detección rtPCR era el mismo que el par de cebadores universales utilizado en el kit SALSA MLPA P095. Las sondas de hibridación para los cromosomas 13, 18 y 21 fueron modificados de la mezcla original del kit P095. Específicamente, el fragmento de relleno fue reemplazado con una secuencia de sonda de detección de unión en el rtPCR. Tal secuencia es común a las ocho sondas de hibridación específicas para un tipo de cromosoma, pero varía con las sondas de hibridación para los diferentes tipos de cromosomas. De acuerdo con este diseño, el tamaño de la sonda de hibridación fue < 80 nucleótidos. De esta forma se pueden detectar simultáneamente las trisomías 21, 18 y 13 en una sola reacción; se investigaron 144 muestras clínicas ciegas incluyendo 32 casos de trisomía 21, 11 casos de trisomía 18, un caso de trisomía 13, y 100 muestras de controles no afectados, comparando los resultados con el análisis de cariotipo. MLPA/rtPCR pudo detectar correctamente todos los casos de trisomía, incluso cuando estaba presente en mosaico, lo que sugiere que este enfoque puede tener aplicabilidad en el diagnóstico prenatal no invasivo con muestras de sangre materna.16 Recientemente, Yan y colaboradores han desarrollado un método de matriz basada en MLPA para la rápida detección de aneuploidías comunes que contiene 116 sondas universales que cubren los cromosomas X, Y, 13, 18 y 21, y 8 genes autosómicos de control denominado array-MLPA. En un estudio ciego de 161 muestras de sangre periférica y 12 muestras de LA previamente estudiadas por cariotipo, estos autores demuestran que el 97.7% de las muestras, incluyendo todas las de LA, fueron identificadas correctamente por array-MLPA. Este estudio evidencia la correcta aplicación y un fuerte potencial de array-MLPA en el diagnóstico clínico y las pruebas prenatales para la detección rápida y sensible de aneuploidías cromosómicas.17
Conclusiones
La MLPA es una técnica reciente en nuestro país para el diagnóstico de las principales aneuploidías; es una prueba que presenta las ventajas de ser más rápida (2.5 días) que el cariotipo (15 días) y de no requerir cultivo celular.
En nuestro estudio se pudo corroborar la utilidad del MLPA en el diagnóstico de los casos con poca viabilidad y por ende baja probabilidad de obtención de cultivo celular adecuado para estudio citogenético.
Debe tenerse en cuenta que el diagnóstico prenatal rápido por MLPA incluye las principales aneuploidías (13, 18, 21, X y Y) pero no puede detectar rearreglos balanceados, mosaicos ni alteraciones que involucren a otros cromosomas.
]]> La experiencia mundial sugiere que es posible aplicar MLPA, bajo los criterios en que fue ideada. Es claro que aún no se debe excluir el cariotipo o FISH, en la intención diagnóstica; sin embargo, MLPA sí representa una alternativa en aquellas muestras en que por fallas en el cultivo celular, cantidad de muestra, o necesidad de resultados rápidos, el cariotipo no pueda llevarse a cabo.
REFERENCIAS
1. Yusuf RZ, Naeem R. Cytogenetic abnormalities in products of conception: a relationship revisited. Am J Reprod Immunol 2004; 52: 88-96. [ Links ]
2. Lomax B, Tang S, Separovic E, Phillips D, Hillard E, Thomson T, Kalousek DK. Comparative genomic hybridization in combination with flow cytometry improves results of cytogenetic analysis of spontaneous abortions. Am J Hum Genet 2000; 66: 1516-21. [ Links ]
3. Hochstenbach R, Meijer J, van de Brug J, Vossebeld-Hoff I, Jansen R, van der Luijt RB, Sinke RJ, Page-Christiaens GC, Ploos van Amstel JK, de Pater JM. Rapid detection of chromosomal aneuploidies in uncultured amniocytes by multiplex ligation-dependent probe amplification (MLPA). Prenat Diagn 2005; 25: 1032-9. [ Links ]
4. Golbus MS, Loughman WD, Epstein CJ, Halbasch G, Stephens JD, Hall BD. Prenatal genetic diagnosis in 3,000 amniocentesis. N Engl J Med 1979; 300: 157-63. [ Links ]
5. Los FJ, van Den Berg C, Wildschut HI, Brandenburg H, den Hollander NS, Schoonderwaldt EM, Pijpers L, Jan HGR, Van Opstal D. The diagnostic performance of cytogenetic investigation in amniotic fluid cells and chorionic villi. Prenat Diagn 2001; 21: 1150-8. [ Links ]
6. Tajiri N, Acosta S, Glover LE, Bickford PC, Jacotte SA, Yasuhara T, Date I, Solomita MA, Antonucci I, Stuppia L et al. Intravenous grafts of amniotic fluid-derived stem cells induce endogenous cell proliferation and attenuate behavioral deficits in ischemic stroke rats. PLoS One 2012; 7: e43779. [ Links ]
7. Willis AS, van den Veyver I, Eng CM. Multiplex ligation-dependent probe amplification (MLPA) and prenatal diagnosis. Prenat Diagn 2012; 32: 315-20. [ Links ]
8. Boormans EM, Birnie E, Oepkes D, Galjaard RJ, Schuring-Blom GH, Lith JM. Comparison of multiplex ligation-dependent probe amplification and karyotyping in prenatal diagnosis. Obstetrics and Gynecology 2010; 115: 297-303. [ Links ]
9. Gerdes T, Kirchhoff M, Lind AM, Vestergaard LG, Kjaergaard S. Multiplex ligation-dependent probe amplification (MLPA) in prenatal diagnosis-experience of a large series of rapid testing for aneuploidy of chromosomes 13, 18, 21, X, and Y. Prenat Diagn 2008; 28: 1119-25. [ Links ]
10. Kjaergaard S, Sundberg K, Jorgensen FS, Rohde MD, Lind AM, Gerdes T, Tabor A, Kirchhoff M. Diagnostic yield by supplementing prenatal metaphase karyotyping with MLPA for microdeletion syndromes and subtelomere imbalances. Prenat Diagn 2010; 30: 995-9. [ Links ]
11. Kooper AJ, Faas BH, Kater-Baats E, Feuth T, Janssen JC, van der Burgt I, Lotgering FK, van Kessel AG, Smits AP. Multiplex ligation-dependent probe amplification (MLPA) as a stand-alone test for rapid aneuploidy detection in amniotic fluid cells. Prenat Diagn 2008; 28: 1004-10. [ Links ]
12. Van Opstal D, Boter M, de Jong D, van den Berg C, Bruggenwirth HT, Wildschut HI, de Klein A, Galjaard RJ. Rapid aneuploidy detection with multiplex ligation-dependent probe amplification: a prospective study of 4,000 amniotic fluid samples. Eur J Hum Genet 2009; 17: 112-21. [ Links ]
13. Slater HR, Bruno DL, Ren H, Pertile M, Schouten JP, Choo KH. Rapid, high throughput prenatal detection of aneuploidy using a novel quantitative method (MLPA). J Med Genet 2003; 40: 907-12. [ Links ]
14. Sellner LN, Taylor GR. MLPA and MAPH: new techniques for detection of gene deletions. Hum Mutat 2004; 23: 413-9. [ Links ]
15. Gerdes T, Kirchhoff M, Lind AM, Larsen GV, Schwartz M, Lundsteen C. Computer-assisted prenatal aneuploidy screening for chromosome 13, 18, 21, X and Y based on multiplex ligation-dependent probe amplification (MLPA). Eur J Hum Genet 2005; 13: 171-5. [ Links ]
16. Guo Q, Zhou Y, Wang X, Li Q. Simultaneous detection of trisomies 13, 18, and 21 with multiplex ligation-dependent probe amplification-based real-time PCR. Clin Chem 2010; 56: 1451-9. [ Links ]
17. Yan JB, Xu M, Xiong C, Zhou DW, Ren ZR, Huang Y, Mommersteeg M, van Beuningen R, Wang YT, Liao SX et al. Rapid screening for chromosomal aneuploidies using array-MLPA. BMC Med Genet 2011; 12: 68. [ Links ]
]]>